Cytoscape使用方法(正式版本)
- 格式:pdf
- 大小:2.12 MB
- 文档页数:28

cytoscape 提取核心处方方法Cytoscape是一款用于生物信息学和计算生物学研究的开源软件,它提供了一种可视化和分析复杂网络的方法。
在生物医学领域中,蛋白质-蛋白质相互作用网络分析被广泛应用于揭示生物体内重要的生物过程和疾病发生机制。
核心处方是一种从蛋白质-蛋白质相互作用网络中提取具有重要功能的亚网络的方法,是研究生态系统中的关键物种和关键蛋白质的重要工具。
在Cytoscape中进行核心处方提取需要以下几个步骤:1. 构建蛋白质-蛋白质相互作用网络:首先,需要从公开的蛋白质-蛋白质相互作用数据库(如STRING、BioGRID等)中获取相关的相互作用数据,并导入到Cytoscape中。
然后,利用Cytoscape提供的网络编辑工具将这些相互作用数据构建成一个网络图。
2. 确定节点重要性指标:为了确定网络中的重要蛋白质节点,我们需要计算每个节点的重要性指标。
常用的指标有度中心性(Degree Centrality)、介数中心性(Betweenness Centrality)、接近中心性(Closeness Centrality)等。
这些指标可以通过Cytoscape中的插件或网络分析工具来计算和显示。
3. 提取核心亚网络:根据节点重要性指标,我们可以选择最重要的节点作为核心节点,并从核心节点开始向外扩展,逐步添加与核心节点相连接的节点,直到满足某种条件(如节点数目、连通性等)。
这样就可以提取到一个具有重要功能的亚网络,即核心处方。
4. 分析核心亚网络:一旦核心亚网络被提取出来,我们可以利用Cytoscape提供的网络分析工具对其进行进一步的分析。
例如,可以计算和显示核心亚网络的网络特征(如平均节点度、连通性、聚集系数等),寻找节点之间的共有模块(如社团检测),进行生物信息学注释(如基因本体注释、通路富集分析等),甚至进行动态网络模拟等。
总之,Cytoscape提供了一种强大的方法来提取和分析核心处方,帮助研究者理解生物体内复杂网络的结构和功能。

cytoscape用法
Cytoscape是一款常用的网络可视化工具,可以用于展示和分析复杂网络数据。
以下是Cytoscape的一些常见用法:
1.导入网络数据:Cytoscape支持导入多种格式的网络数据,包括sif、
csv、txt、xml、json等。
可以通过菜单栏中的File菜单或者Plugins 菜单导入数据。
2.创建网络:如果还没有现成的网络数据,可以使用Cytoscape的
图形界面创建一个新的网络。
在菜单栏中选择New菜单,可以创建一个空的或者基于现有网络的网络。
3.编辑网络:通过Cytoscape的图形界面,可以对网络进行编辑,
包括添加/删除节点、添加/删除边、修改节点/边的属性等。
可以通过菜单栏中的Edit菜单进行编辑。
4.可视化网络:Cytoscape提供了多种可视化网络的方式,包括布局、
颜色、形状、大小等。
可以通过菜单栏中的View菜单进行可视化设置。
5.分析网络:Cytoscape提供了多种网络分析工具,包括网络拓扑分
析、社区发现、网络中心度等。
可以通过菜单栏中的Analyze菜单进行分析。
6.插件管理:Cytoscape支持通过插件扩展其功能,可以通过Plugins
菜单安装和管理插件。
总之,Cytoscape是一款功能强大的网络可视化工具,可以用于展示
和分析复杂网络数据,支持多种数据格式导入、可视化设置、网络分析和插件扩展等功能。
![[重磅]手把手教你玩Cytoscape](https://uimg.taocdn.com/5fc38b8b70fe910ef12d2af90242a8956becaae4.webp)
[重磅]⼿把⼿教你玩Cytoscape⾮常感谢北京协和医学院药⽤植物研究所于猛⽼师的分享。
在这个看颜值的世界,⼀张狂拽酷炫的图不仅有助于解释⽂章的精髓,更能吸引审稿⼈和读者的眼球。
随着⾼通量多组学的兴起,数据分析与整合、以及可视化变得越来越重要。
今天omicsPie将⼿把⼿教你玩Cytoscape!当然,Cytoscape软件的功能⾮常强⼤,本次只针对我们常⽤的关联分析可视化进⾏了整编。
⼀⼝吃不成⼤胖⼦,那都得天天吃。
Learning by doing,且⾏且珍惜!别忘了转发评论点赞打赏,这才对得起于⽼师和⼩编的⾟苦啊!(结尾有彩蛋,⾃⼰慢慢体会)Ready, Go!C. Zhang et al. / EBioMedicine 2 (2015) 968–984⼩伙伴们阅读⽂献看到这样炫酷的关联图时,您是否眼前⼀亮?其实这样的图可以通过很多软件来实现,⽐如Gephi, R, Cytoscape……下⾯我们⼀起⽤最短的时间学习⼀下怎样⽤Cytoscape软件做关联图吧!Cytoscape简介Cytoscape是⼀款图形化显⽰⽹络并进⾏分析和编辑的软件,它⽀持多种⽹络描述格式,也可以⽤以Tab制表符分隔的⽂本⽂档或Microsoft Excel⽂件作为输⼊,或者利⽤软件本⾝的编辑器模块直接构建⽹络。
软件官⽹:/各版本下载地址:/download_old_versions.htmlCytoscape的核⼼是⽹络,最简单的⽹络图包括节点(node)和边(edge)。
节点是你的关联变量,可以是基因、蛋⽩,代谢物质或者miNRA等等;节点与节点之间的连接 (edge) 代表着这些变量之间的相互作⽤。
⼀张简单的⽹络结构,⽐如下图。
但是想要拥有CNS级别的⾼⼤上,就需要下功夫了!格式(⾮常重要)关联数据格式(⾮常重要)Cytoscape关联数据正所谓条条⼤路通罗马,有很多种⽅法可以编辑数据集,数据关联格式也并⾮唯⼀,现在介绍给⼤家的是⾃认为⽐较⽅便的⼀种格式。

生物信息学分析工具的使用教程导言:在生物学领域中,随着高通量测序技术的快速发展,生物信息学分析工具的应用变得越来越重要。
这些工具能够帮助研究人员进行基因组、转录组、蛋白质组等大规模数据的分析和解释。
本文将为您介绍几种常用的生物信息学工具,并提供详细的使用指南。
一、BLAST(基因序列比对工具)BLAST(Basic Local Alignment Search Tool)是最常用的生物信息学工具之一,用于比对基因或蛋白质序列中的相似性。
以下是使用BLAST的步骤:1. 打开NCBI网站的BLAST页面,并选择适当的BLAST程序(如BLASTn、BLASTp等)。
2. 将查询序列粘贴到"Enter Query Sequence"框中,或者上传一个FASTA格式的文件。
3. 选择适当的数据库,如"nr"(非冗余序列数据库)或"refseq_rna"(已注释的RNA序列数据库)。
4. 设置相似性阈值、期望值和其他参数。
5. 点击"BLAST"按钮开始比对。
6. 结果页面会显示比对结果的列表和详细信息,包括匹配上的序列、相似性得分等。
二、DESeq2(差异表达基因分析工具)DESeq2是一种用于差异表达基因分析的R包。
以下是使用DESeq2的步骤:1. 安装R语言和DESeq2包。
2. 将基因表达矩阵导入R环境中,并进行预处理(如去除低表达基因)。
3. 根据实验设计设置条件和组别。
4. 进行差异分析,计算基因的表达差异和显著性。
5. 可视化差异表达基因的结果,如绘制散点图、MA图、热图等。
三、GSEA(基因集富集分析工具)GSEA(Gene Set Enrichment Analysis)是一种基于基因集的富集分析方法,用于识别与特定性状或实验条件相关的生物学功能。
以下是使用GSEA的步骤:1. 准备基因表达矩阵和相关的分组信息。


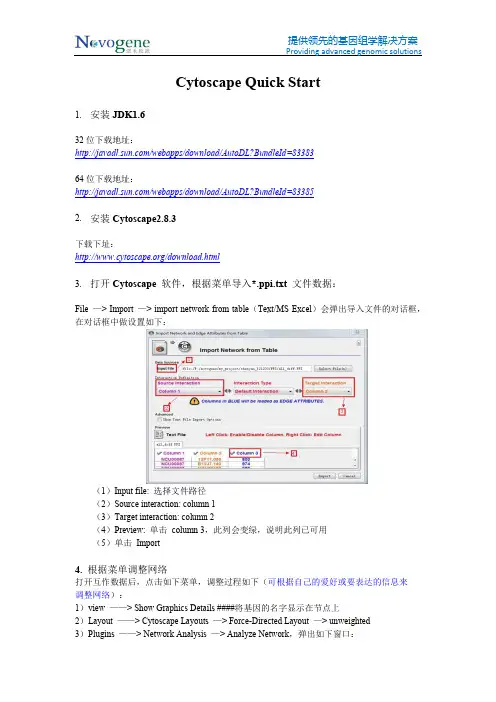
Cytoscape Quick Start1.安装JDK1.632位下载地址:/webapps/download/AutoDL?BundleId=8338364位下载地址:/webapps/download/AutoDL?BundleId=833852.安装Cytoscape2.8.3下载下址:/download.html3.打开Cytoscape 软件,根据菜单导入*.ppi.txt 文件数据:File —> Import —> import network from table(Text/MS Excel)会弹出导入文件的对话框,在对话框中做设置如下:(1)Input file: 选择文件路径(2)Source interaction: column 1(3)Target interaction: column 2(4)Preview: 单击 column 3,此列会变绿,说明此列已可用(5)单击 Import4. 根据菜单调整网络打开互作数据后,点击如下菜单,调整过程如下(可根据自己的爱好或要表达的信息来调整网络):1)view ——> Show Graphics Details ####将基因的名字显示在节点上2)Layout ——> Cytoscape Layouts —> Force-Directed Layout —> unweighted3)Plugins ——> Network Analysis —> Analyze Network,弹出如下窗口:4)如图所选,Treat the network as undirected —> OK ,会弹出如下窗口:5)如上图,点击 Visualize Parameters(用户也可了解网络的其他属性,如Node Degree Distribution 等,具体信息和意义可以参考cytoscape 的在线帮助或联机帮助),弹出如下图:(1)Map node size to: degree(2)Map node color to: Clustering Coefficient(3)Map edge size to: column 35. 结果说明互作网络中节点(node)的大小与此节点的度(degree)成正比,即与此节点相连的边越多,它的度越大,节点也就越大。

Cytoscape史上最全攻略今天还是讲Cytoscape,虽然已经写了很多相关的⽂章,但是依然有童鞋在问哪⾥可以下载Cytoscape这样没有营养的问题,这让本宫⽆⽐⽆⽐的痛⼼!!!所以今天本宫会很详细、⾮常详细、巨详细、史⽆前例地详细、前⽆古⼈,后⽆来者地详细讲解如何使⽤Cytoscape。
Cytoscape是⽤于可视化⽹络数据的⼀个⾮常强⼤的⼯具,⽐如说表现⼀组基因间的相互关系,数据的表现⼒上孰优孰劣⼀⽬了然。
⽂本形式和⽹络图形式,在数据的表现⼒上点(node)和线(edge)是⽹络图的两个核⼼要素。
我们做各种各样的⽹络图,归根结是⽹络图的两个核⼼要素。
我们做各种各样的⽹络图,归根结底是对图中的点和线进⾏注释,我们通过改变点和线的样式来对点和线赋予各种各样的信息,从⽽实现数据的可视化。
息,从⽽实现数据的可视化很多童鞋可能在下载这⼀步就放弃了,因为下载速度可能会很慢,200M的宽带可能只有2kb的见⽂末⽹盘链接)。
下载速度。
本宫送佛送到西,翻过去给你们把⽕种带回来(见⽂末⽹盘链接)安装的时候先安装java,安装好了之后需要设置环境变量在环境变量中,要修改两个地⽅,⼀个是添加JAVA_HOME。
选择“新建”,变量名填上JAVA_HOME,变量值填上C:\Program Files\Java\jdk1.8.0_151,在java的安装过程中,默认⼀直下⼀步安装,所以装在C盘,如果你在安装过程中改了,那可能是D盘或者E盘,那么变量值要做相应的更改。
还要修改⼀个地⽅,就是Path,添加JAVA的变量值到Path中,选择Path,然后点“编辑”,在最后⾯添加如下语句;%JAVA_HOME%\bin;打开命令提⽰符cmd,输⼊java -version,如果能正常显⽰,那表明装好了,你就可以装Cytoscape了虽然⽹盘⾥的是最新版本3.60,但是不知道重新安装需不需要重新下载插件什么的,时间所如果⼤家在使⽤过程中发现什么差别,请在迫,今天给⼤家所做的演⽰都是基于3.42版本,如果⼤家在使⽤过程中发现什么差别,请在⽂末留⾔。

科研实验中的生物信息学工具使用教程生物信息学是将数学、统计学和计算机科学应用于生物学研究的交叉学科。
在现代科研中,生物信息学工具已经成为了生物学实验和研究的重要组成部分。
本文将介绍几种常用的生物信息学工具,并提供详细的使用教程。
1. BLAST(Basic Local Alignment Search Tool)BLAST是生物信息学领域中最常见的工具之一,用于在数据库中快速比较DNA或蛋白质序列的相似性。
以下是使用BLAST进行基本比对的步骤:(1)打开NCBI网站,并进入BLAST页面。
(2)选择“nucleotide”或“protein”,取决于你要比对的序列类型。
(3)复制粘贴或上传你要比对的序列。
(4)选择合适的数据库进行搜索,如“nr”(非冗余数据库)。
(5)点击“BLAST”按钮,等待搜索结果。
BLAST会为你提供一个比对报告,其中包含了与你的查询序列相似的序列列表。
2. EMBOSS(European Molecular Biology Open Software Suite)EMBOSS是一个开源的生物信息学软件包,提供了一系列用于序列分析和比对的工具。
以下是使用EMBOSS进行序列分析的步骤:(1)打开EMBOSS软件(可以下载并安装在你的计算机上)。
(2)选择合适的工具,如“water”(Smith-Waterman比对算法)。
(3)输入查询序列和数据库序列。
(4)设置相关参数,如匹配分数和距离惩罚。
(5)点击“Run”按钮,等待分析结果。
EMBOSS将为你提供一个比对报告,并给出一些统计数据,如匹配分数和最佳比对。
3. R/BioconductorR是一种统计软件和编程语言,Bioconductor是R语言的一个生物信息学扩展包,提供了丰富的生物信息学工具和分析方法。
以下是使用R/Bioconductor进行基因表达分析的步骤:(1)打开R软件并加载Bioconductor包。

Cytoscape的使用方法(带图片解析)最近在做网络构建的课题,用到了cytoscape软件,所以把软件的用法总结了一下。
cytoscape是由许多研究单位共同合作开发的一个开放源码的生物信息分析软件。
研究单位包括加州大学圣地亚哥分校的Trey Ideker 实验室,加州大学旧金山分校的Bruce Conklin实验室,Pasteur研究院的Benno Schwikowski实验室,Memorial_Sloan-Kettering癌症研究中心的Chris Sander实验室,Institute forSystems Biology的Leroy Hood实验室。
首先这个软件是基于JAVA的一款多功能软件,在安装好相应版本的JAVA之后,安装的cytoscape才可以正常运行。
一、输入文件支持多种输入格式,可以保存工程文件,支持多种布局的方式,支持导出图像,样式可以做丰富的调整,智能的选择过滤。
1、 edge文件格式:tsv(制表符分隔的txt是一样的),csv(逗号分隔的),xls,xlsx文件等,一般两种tsv文件就足够我们使用了。
下面就是一个典型的三列tsv格式的文件示例,第一列是原节点,第三列是目标节点,第二列是两者的相互作用关系,这里的作用关系标示了不同类型,在后面的网络设置中大家可以看到它的妙处,而这里的source与target都是数字,怎样转换为我们想看到的基因名字呢,这里也是先留一个问题,后面解释。
figure 12、 node属性文件figure 2可以导入,可以用来解决我们上面的问题,将edge文件中的数字替换成可视化的简单的基因名字。
二、导入数据打开软件之后出现如下界面:figure 3可以点击上面的物种名字选择一个实例来学习,也可以直接选择空的network用来导入数据,例如我选择了Arabidopsis,就出现了如下的界面,图示的是一个已经做好的网络的例子:figure 4用户界面:figure 5(来自网络) 1、导入数据figure 6figure 7(来自网络)2、导入属性文件figure 8figure 9(来自网络)3、布局figure 10三、高级功能1、调整样式(1)基本样式figure 11figure 12(2)节点样式figure 13figure 14figure 15(来自网络)(3)边样式figure 16figure 17figure 18(来自网络)2、改节点名称figure 19 (来自网络) 3、改边的颜色figure 20(来自网络)4、调控网络各项指标统计figure 21得到的结果会出现在一个新的面板当中:figure 225、改变节点大小这里需要强调很重要的一点是,在对这里的改变节点大小进行操作之前,如果是想通过节点连接的边的数量进行梯度设定的话,是必须要进行上面第四步的统计分析的,否则没有Degree选项出现:figure 23(来自网络)双击上面梯度设置的区域可以出来控制面板进行修改:figure 24四、选择过滤1、节点的选择节点的选择可以通过将目标节点放在一个文件中导入,如果节点数少的话可以手动点选:figure 252、子网络的选择与分离再将节点点选之后,如果想把其与大网络分离的话就点击菜单的图标栏里倒数第四个图标,就可以得到下面第二张图的结果:figure 26figure 27六、导出图片数据的导出可以是网络文件,表格文件或者是图片文件,图片文件包括多种图片格式以及pdf格式,对比图标的形态,下图所示的左侧两个是快速导入文件的图标:figure 28七、表达分析Cytoscape还可以导入基因的表达值,将不同的表达值进行颜色的梯度展示,由于我的分析没有这部分数据所以将网络上学到的图片做了几个截图:figure 29figure 30figure 31figure 32figure 33figure 34figure 35figure 36figure 37figure 38figure 39八、还有什么Cytoscape提供了很多外接的数据库,右键点击相应节点,出现的选项里面选择externallinks,里面有以下所示连接的数据库:figure 40此外,基于大量功能强大的插件的开发,以下的功能也很全面:GO分析:BiNGOPathway分析:CytoKegg、KEGGscape等模块与复合物分析:jActiveModules+BiNGO。
Cytoscape⼗讲之下载安装及使⽤Cytoscape⼗讲之⽹络图的认知Cytoscape的功能集中于两点,⼀个是展⽰蛋⽩/其他features间的⽹络图,⼀个使⽤app⾥的⼩⼯具分析,界⾯操作性相对简单(肯定⽐PS简单)。
软件最好更新⼀下,因为不同软件版本,相同按钮的软件中的位置不太⼀样。
直接点击Download 3.7.1,可以下载最新版本。
软件有点⼤,⼏百M。
JAVA安装:java8是否已安装?如果没有安装或环境变量的配置等,安装Cytoscape时候点击提⽰出:是否安装java,点击是即可。
其他默认安装就可以,可以更改安装⽬录。
(但不建议瞎改)如图。
open source:可以找到不同系统(mac/Linux/Wins)释放的不同版本Release Notes:找到释放的不同版本Samples Visualizations:展⽰出软件可视化图的类型,让你看看不同版本,软件能做什么图cytoscape-tutorials:重点!Cytoscape manual:可以查看Cytoscape的⽹页端学习⼿册Cytoscape YouTube channel:你们可以试试能不能打开Documentation for users:可以获得更多学习材料,如3.x PDF Version:本地下载帮助⼿册,⽬前3.6版本的⼿册249页(⾃学)其他软件内启动Cytoscape等Cytoscape 的核⼼是⽹络,简单的⽹络图包括节点(node)和线/边/连接(edge)。
全部适⽤于点/线的参数,我们可以称之为默认参数。
根据某些属性调节的参数带来的渐变或者离散的变化(这个属性,你可以在⽂件中⾃⼰添加⼀列)。
选中某些/个/条调节后适⽤的变化,如特定⼀条线型需要设置为波浪线。
节点:就是线线焦点 形状:圆型、正⽅形等 填充:Fill color ⾼度:Height 宽度:Width边界:节点周围是否再涂边,⽐如⼀个圆,如果边界线全是灰⾊实线,现可调整为不同粗细线,不同颜⾊线,不同形状线条的属性。
Cytoscape2.6使用手册郑国毅译目录目录 (1)一、Cytoscape介绍及其安装的一些要求: (2)Cytoscape2.6的新特点 (2)Cytoscape的安装 (3)系统性能的要求 (3)安装过程 (3)开始应用 (3)内存的消耗说明 (4)栈的大小分配 (4)Cytoscape的界面 (5)菜单 (6)File(文件) (6)Edit(编辑) (7)View(视图) (7)Select(选择) (7)Layout(布局) (7)Plugins(插件) (8)Help(帮助) (8)二、入门Cytoscape (9)三、Cytoscape中基本的数据表达分析 (16)一、Cytoscape介绍及其安装的一些要求:Cytoscape是一个专注于开源网络可视化和分析的软件。
它的核心是提供基础的功能布局和查询网络,并依据基本的数据的结合成可视化网络。
它可以通过插件扩展的,为了适应快速发展的附加的计算分析和和其他功能。
他最先用于生物学,为了整合分子间相互作用的网络(高复杂的,和其他的分子状态信息)。
虽然适应任何分子系统的结构和相互关系。
他是非常强大的,在于联合大的数据库(蛋白质,DNA,和对人类和生物日益重要的遗传)。
Cytoscape允许可视化的网络与文件,显型,其它分子状态信息,和链接网络到功能注释。
Cytoscape的重要组织方式是网络,因子,蛋白质和分子用点表示,两点间的交互关系用链接也就是边Cytoscape的发展Cytoscape软件是由以下的机构联合完成的:Institute for Systems Biology (Leroy Hood lab), theUniversity of California San Diego (Trey Ideker lab), Memorial Sloan-Kettering Cancer Center (ChrisSander lab), the Institut Pasteur (Benno Schwikowski lab), Agilent Technologies (Annette Adler lab) andthe University of California, San Francisco (Bruce Conklin lab).可以访问 得知详细情况许可Cytoscape是受the GNU LGPL (Lesser General Public License)保护的。
Tutorial:Basic Expression Analysis in Cytoscape-HumanSlideshow Basic Expression Analysis in Cytoscape (30 min)Handout Basic_Expression_Analysis_in_Cytoscape-Human.pdf (11 pages)Tutorial Curators Kristina Hanspers, Alex Pico, Mike SmootContents[hide]∙ 1 Loading Network∙ 2 Loading expression data∙ 3 Visualizing Expression Datao 3.1 Set the node coloro 3.2 Set the default node coloro 3.3 Set the node shapeo 3.4 Set the node border∙ 4 Data analysis featureso 4.1 Filter Nodeso 4.2 Search for a nodeo 4.3 Exploring NodesCytoscape is an open source software platform for integrating, visualizing,and analyzing measurement data in the context of networks. This tutorial will introduce you to:▪Combining data from two different sources: experimental data in the form of microarrray expression data and network data in the form of interaction data.▪Visualizing networks using expression data.▪Filtering networks based on expression data.Loading Network▪Start Cytoscape and load the network File:HumanInteractome subset.sif.▪Apply the force-directed layout to organize the layout of the nodes. Select the "Layout->Cytoscape Layouts->Force-Directed Layout" menu.▪The network should now look similar to this:Loading expression data▪Download File:Pellegrini et al Data.txt.zip expression data and unzip it.▪Using your favorite text editor, open the file Pellegrini_et_al_Data.txt. The first few lines of the file are as follows:Gene Symbol Entrez id Probeset CREB kd control p value fold change Sign CREB bindingA2M 2 217757_at 42.24 57.450.4 1.5 yesA2ML1 144568 1553505_at 67.95 206.470.11 0.58A2ML1 144568 1564307_a_at 160.05 183.440.81 0.95You should note the following information about the file:1. The first line consists of labels.2. All columns are separated by a single tab character.3. The first column contains node names, and must match the names of the nodes in yournetwork exactly!4. The second column contains Entrez Gene IDs.5. The third column contains Affymetrix probe set IDs. This column is optional, and the data isnot currently used by Cytoscape, but this column may be useful for analysis in othermicroarray analysis tools.6. The remaining columns contain experimental data; average expression for experimentaland control groups, p value and fold change for the comparison, and data on whether ornot the gene binds CREB. See the manuscript for details on the data generation. NOTE: The expression data used in this example has been pre-processed to work with the interaction network used. The data is a composite of data files from Pellegrini et al, BMC Cancer, 2008.▪Under the File menu, select Import → Attribute from Table (Text/MS Excel).▪Click "Node" for the type of attribute to import.▪Select the file Pellegrini_et_al_Data.txt.▪Click the "Text File Import Options" check box.▪Make sure the "Tab" check box in the "Delimiter" section is selected and that no other check box under "Delimiter" is selected. The preview should indicate that it is importing multiplecolumns of data.▪Click the "Transfer first line as attribute names" check box in the "Attribute Names" section. The preview should now show be using the first row of the input file as column names and the import window should look like the image below.▪Click the "Import" button to import the attribute data.Now we will use the Node Attribute Browser to browse through the expression data, as follows. ▪Select a node on the Cytoscape canvas by clicking on it.▪In the Node Attribute Browser, click the Select Attributes button , and select the attributes "fold change" and "p value" by left-clicking on them. Right-click to close the menu. ▪Under the Node Attribute Browser, you should see your node listed with their expression values, as shown.Visualizing Expression DataProbably the most common use of expression data in Cytoscape is to set the visual attributes of the nodes in a network according to expression data. This creates a powerful visualization, portraying functional relation and experimental response at the same time. Here, we will walk through the steps for doing this.Set the node color▪Double-Click the Node Color row in the Visual Mapping Browser in the Unused Visual Properties Section.▪This action will move Node Color to the top of the Visual Mapping Browser.▪Click the "Please select a value!" cell in the Node Color section.▪This will produce a drop-down menu of available attribute names. Select "fold change".▪Click the "Please select a mapping" cell in the Node Color section.▪This will produce a drop-down menu of available mapping types. Select "Continuous Mapping". ▪This action will produce a basic black to white color gradient.▪Click on the color gradient to change the colors. This will pop-up a gradient editing dialog.▪Drag the left-most, red handle along the top of the gradient. Drag it to an Attribute Value of approx. -1.2▪Drag the white handle to approx 0.5. You can type the Attribute Value in the Handle Settings section to be more precise.▪You can also change the color of each handle by double-clicking or using the Node Color selector button in the Handle Settings section.▪This should produce a Red-White-Green Color gradient like the image below, with min and max extremes colored black and blue, respectively.▪Click 'OK' to save the gradient adjustment dialog and verify that the nodes in the network reflect the new coloring scheme.Set the default node colorNote that the default node color of pink falls within this spectrum. A useful trick is to choose a color outside this spectrum to distinguish nodes with no defined expression value and those with slight repression.▪Click the Defaults network icon in the VizMapper panel.▪Click the Node Color entry and choose a dark gray color.▪Zoom out on the network view to verify that a few nodes have been colored gray.Set the node shapeWe imported both a fold change value and a p value for the comparison between CREB kd and control cells. We can use the p values to change the shape of the nodes so that measurements we have confidence in appear as squares while potentially bad measurements appear as circles.▪Double-Click the Node Shape row in the Visual Mapping Browser in the Unused Visual Properties Section.▪This action will move Node Shape to the top of the Visual Mapping Browser.▪Click the "Please select a value!" cell in the Node Shape section.▪This will produce a drop-down menu of available attribute names. Select "p value".▪Click the "Please select a mapping" cell in the Node Shape section.▪This will produce a drop-down menu of available mapping types. Select "Continuous Mapping". ▪This will create an empty icon in the "Graphical View" row of the Node Shape section. Click on this icon.▪This action will pop-up a continuous shape selection dialog.▪Click the Add button.▪This action will split the range of values with a slider down the middle with a node shape icon to either side of the slider.▪Double-Click on the left node icon (a circle).▪This will pop-up a node shape selection dialog.▪Choose the Rectangle shape and click the Apply button.▪The continuous shape selection dialog should now show both a square and a circle node shape icon.▪Click on the black triangle and move the slider to the left, to slightly lower that 0.05, our threshold for significance.▪Close the continuous shape selection dialog and verify that some nodes have a square shape and some nodes have a circular shape.Set the node borderWe can use the node border color and style to reflect whether a node has been found to be significantly bound by CREB (ref). This data is already available in the dataset as an attribute.▪Double-Click the Node Border Color row in the Visual Mapping Browser in the Unused Visual Properties Section.▪This action will move Node Border Color to the top of the Visual Mapping Browser.▪Click the "Please select a value!" cell in the Node Border Color section.▪This will produce a drop-down menu of available attribute names. Select "Sign CREB binding". ▪This will produce a drop-down menu of available mapping types. Select "Discrete Mapping". ▪This will create a new row for the value "yes", which is the only value available for this attribute.Click on the empty cell to the right of "yes", and then click on the square icon that appears.▪ A color chooser will appear. Pick a color that will stand out against the color scheme, for example a bright yellow. The relevant nodes in the network will be outlined in yellow.Next, we want to also change the border thickness, since the thin yellow border can be hard to see.▪Double-Click the Node Line Width row in the Visual Mapping Browser in the Unused Visual Properties Section.▪This action will move Node Line Width to the top of the Visual Mapping Browser.▪Click the "Please select a value!" cell in the Node Line Width section.▪This will produce a drop-down menu of available attribute names. Select "Sign CREB binding". ▪This will produce a drop-down menu of available mapping types. Select "Discrete Mapping". ▪This will create a new row for the value "yes", which is the only value available for this attribute.The default node border width of 1.5 will be selected to the right of "yes".▪Click in the box specifying the width and type 5.▪Zooming in to part of the network, it now looks like this:Data analysis featuresThis section presents a few examples of features in Cytoscape that can be used to further analyze the network and associated data.First, here is some background on your data. The data is from an experiment in a human myeloid leukemia cell line. The cAMP Response Element Binding Protein, CREB, was knocked down by shRNA and the expression profile of knockdown cells was compared to that of control cells from the same cell line. See Pellegrini et al.Filter NodesIt is possible to filter any network in Cytoscape based on either node or edge attributes. Here, we filter the network based on high and low fold change between the two groups.▪Click the Filters tab in the Control Panel.▪Click the Attribute/Filter chooser in the Filter Definition and choose "node.fold change".▪Click the Add button in the Filter Definition section to add the selected attribute to the filter. ▪This action will create a slider for the fold change in the filter.▪Double-click on the slider to select cutoffs. Set the low bound to 2 and click OK.▪Now, expand the selection to first neighbors of selected nodes byclicking Select→Nodes→First Neighbors of Selected Nodes.▪Create a new network by clicking New→Network→From Selected Nodes, All Edges.▪Apply a force-directed layout to the new network by selecting Layout → Cytoscape Layouts → Force-Directed Layout.▪Navigate to the Network tab in the Control Panel. Rename the new network by right-clicking on it and selecting Edit Network Title. Type in "upregulated".▪The new network should now look like this:▪Repeat the Filter for down-regulated genes with fold change under 0.5. Name the second subnetwork "downregulated".▪The "downregulated" network should look like this:Search for a nodeWe will now search for the CREB1 (CREB) node in the network.▪In the toolbar, to the right of the Search box, click the icon for Configure search options'.▪In the dialog that opens, select the radio button for Nodes and make sure Unique Identifier is selected in the drop-down. Click Apply.▪In the search field, type in "CREB". In the list of hits that is generated, you will see that there is one node named CREB1, which is an alias name for the CREB transcription factor. Select this node from the list and click Enter.▪The CREB node will be highlighted in the network.▪To make it easier to explore the interactions immediately surrounding CREB, we can create a network based on the first degree neighbors of CREB by clicking Select → Nodes → First Neighbors of Selected Nodes.▪ A set of nodes should now be highlighted. Click File → New → Network → From Selected Nodes, All Edges. A new network will be produced.▪Clean up the network by applying a force-directed layout.▪The network should now look like this:▪By examining the network, we can see that CREB interacts with both up- and down-regulated nodes. CREB is known to act both as a transcriptional repressor and transcriptional activator. If you search for CREB in the two subnetworks representing all up- and down-regulated nodes respectively, you will see that CREB is present in both networks.Exploring Nodes▪In the "HumanInteractome_subset" network, right click on the node CREB1.▪Select the menu LinkOut → Entrez → Gene.▪This action will pop-up a browser window and search the Entrez Gene database for CREB.。
Cytoscape软件画图说明
1、画图前,先准备两个输入文件。
2、打开cytoscape软件,导入数据。
导入edge、txt文件
点击----Network
点击ok得到原始图形节点1,文件中第
一列
节点2,文件中
第2列
连接类型,文件
中第3列
点击layout ----Apply Preferred Out 改变图形排列方式
此处可以用鼠标在画布中拖动图形到合适得位置。
改变画布背景。
点击左侧Contro Panel ----Style---network ---Backgroud paint
设置节点之间连线得宽度与颜色Contro Panel ----Style---Edge
导入node、txt个文件点击----Table 宽度颜色
设置节点图形属性
Contro Panel ----Style---Node
1、node大小
通过设置Height与Width来控制大小
2、Node性状
通过设置Shape来控制
3、Node填充色
通过设置Fill Color来控制
4、Node标签得设置
点击Properties -- Label Position
点击Label Position来设置标签位置。
这里就是一个示范操作,要细致调整标签位置还就是要设置Column与Mapping Type两个参数。
设置完成之后图形
调节节点之间得距离
点击layout ----Scale
最后,
画图导出成pdf文件
点击View as Graphics
鼠标拖动。
Cytoscape中文教程(1)写在前面:•对于我们大多数来说,用图形或图表更比数据本身更能说明问题,更容易让人理解,并且可以赏心悦目。
细胞内部,大量的分子时刻都在发生着变化或相互作用。
对于我们来说,了解这种相互作用是非常重要的。
但就像中国地图,如果抽象的描述东部的东部是谁,一定让人头大,但如果在地图上指出来那效果是完全不一样的。
cytoscape 就给我们提供了一种这种分子地图的可能性,即蛋白互作网络,当然这种网络可以由多种定义形式来产生,比如染色体物理位置,比如共表达性质等;也可以产生多种排布形式(看个人需要)。
所以我觉得这是一个必备的技能,不只会出图,更要会知道出什么样的图,怎么解释这种图。
这样就需要知道作图背后的知识。
所以我翻译并加了自己的理解注释,完成了这份手册。
•这个手册真的有点长,是我早期翻译的,如果你完全不懂Cytoscape,那么你读这些,应该会做出非常漂亮的各种基于cytoscape及插件的图,因为这个教程真的很白。
•cytoscape有很多非常优秀的app,关于cytoscape本身的使用方法完成后,我会稍后发布几个app的使用。
当然,关键还是知道用哪个插件,为什么用,结果怎么解读,其生物学意义是什么。
•原文地址直接从第三部分开始3 命令行参数Cytoscape可以识别很多可选的命令行参数,包括network,节点,边和会话文件等数据文件运行规范,这些文件是可以输出的(有h 或help flag)usage: cytoscape.{sh|bat} [OPTIONS]-h,--help Print this message.-v,--version Print the version number.-s,--session <file> Load a cytoscape session (.cys) file.-N,--network <file> Load a network file (any format).-P,--props <file> Load cytoscape properties file (Java propertiesformat) or individual property: -P name=value.-V,--vizmap <file> Load vizmap properties file (Cytoscape VizMapformat).-S,--script <file> Execute commands from script file.-R,--rest <port> Start a rest service.任何一个指定的文件,都可以被定义为一个路径或URL,例如,你可以指定一个文件为一个网络(假如文件在当前的工作目录存在)cytoscape.sh -N myNet.sif注意:假如文件路径下还有空间,确定在它旁边还要有quotescytoscape.bat -N "C:\Program Files\Cytoscape\sampleData\galFiltered.sif"也可以把一个URL指定为一个网络cytoscape.sh -N [/myNet.sif](/myNet.sif).4 Quick Tour of Cytoscapeimage.png•椭圆形的menu Bar,可以在每个菜单下看详细信息•矩形标记的T ool Bar,有最常用的图标。
Cytoscape基础教程笔记part one昨天开始学用Cytoscape,其tutorial分为两个部分,基础的和高级的。
基础教程又分成了四课:Getting Started、Filters & Editor、Fetching External Data和Expression Analysis。
为防忘记,做个摘记。
第一课新手上路,地址见http://goo.gl/FJLxp。
Cytoscape 可以本地安装,也可以web start。
软件得用java,所以要装JRE。
我在Ubuntu下装了OpenJDK,可以运行。
因为以前一直没把jnlp文件和java关联起来,所以从没成功web start过,试了一下“课文”里给出的链接,似乎不太靠谱,总之是没法启动。
启动Cytoscape后,得下载两个样例文件。
以sif为后缀名的是蛋白相互作用网络信息,里面的蛋白以数字形式区别,以na为后缀名的是各数字id的注释,似乎两者的文件名必须相同才能关联起来。
sif 文件的打开\导入有两种方式:File → Import → Network(Multiple File Types)或者直接Ctrol+L,na文件是File → Import → Node Attributes。
Network导入之后有多种显示风格,2.8版默认风格下,圆圈是各蛋白,称为节点(node),其间各线为edge,代表相互作用。
点中圆圈就选中了一个节点,想要多选,可以采用同时按Shift的方法,也可以先在Select → Mouse Drag Selects设置好选node还是选edge,然后鼠标拖放,一选一大片。
此外还可以有目的地选择。
比如可以Select → Nodes → By Name,然后输入蛋白id,即可选中此节点。
大海捞针即告完成。
此操作的快捷键是Ctrl+F。
如果已经选中了节点,还可以Select → Nodes → First neighbors of selected nodes,可将所选蛋白的直接相互作用蛋白选中,再选File → New → Network → From selected nodes, all edges,即将相互作用网络的一个子网络剥离出来。
Cytoscape软件画图说明1、画图前,先准备两个输入文件LA edge.txt node.tMt2、打开cytoscape 软件,导入数据 导入edge.txt 文件点击 File ----Import ----Network<New S HE .kmFile Edit View Select La^otA Apps Toe Is Help|b| — _—L PiiTi nn^r TableClrlHOntology .nd Arncration.Recent NewOPW-F CtHtO AmFUlfV.FtwcincCH*SCtrl+S-hift-i-SImportExpertTatis:- P-3"- elie第一列OTE5S连接类型,文件umm. Right CNck EdM ColumnTit-Trfl'iil D* □ BO Kc j di节点2,文件中 IliTipcrt NteSwcrk [From Table-[Hecwork「币h> 和、辿•阿却节点1,文件中 杯* kknlllr第2列~r>rg#tColumn 174*Coldiron 3利4>COlMfflfl 2 v 1Tnr*r*frnB S^IJFC tC&iurmt irt BL14F Wi^b^固!•« FI*Lvn Click: Enabltmn :avT ■! 1«Acidimicrcbna* nodvz4Baoteri*# link PPAcitio-tacc ・口・14Bictena PPHlolophiagaltf 4Bacteria PP SQlibacterailesi 4Bact$rid PP Achd-cbj£t»ni« BJCtarn PP Acidlmlicroit>iai»&^Bacteria PPAcldoOacle Hales4BactenaPPAcIfinabAGEanldi 4Qd>Ltvr4d PPdAniruil-ULnLalav. dAantAru —1AilMaiWHlI吕kr« I »xt ? L L » Inf CT n Dp !:□ coi^中第3歹U点击ok 得到原始图形 戶 右■■ '->■ •■■■—” I***# *CT1- Ab」 口 V 仝暮r 护莎.F 匕比M规4命 ,.■ ■; :4.・・・D N I = T#—点击layout ----Apply Preferred Out 改变图形排列方式 此处可以用鼠标在画布中拖动图形到合适的位置。
Cytoscape2.6使用手册郑国毅译目录目录 (1)一、Cytoscape介绍及其安装的一些要求: (2)Cytoscape2.6的新特点 (2)Cytoscape的安装 (3)系统性能的要求 (3)安装过程 (3)开始应用 (3)内存的消耗说明 (4)栈的大小分配 (4)Cytoscape的界面 (5)菜单 (6)File(文件) (6)Edit(编辑) (7)View(视图) (7)Select(选择) (7)Layout(布局) (7)Plugins(插件) (8)Help(帮助) (8)二、入门Cytoscape (9)三、Cytoscape中基本的数据表达分析 (16)一、Cytoscape介绍及其安装的一些要求:Cytoscape是一个专注于开源网络可视化和分析的软件。
它的核心是提供基础的功能布局和查询网络,并依据基本的数据的结合成可视化网络。
它可以通过插件扩展的,为了适应快速发展的附加的计算分析和和其他功能。
他最先用于生物学,为了整合分子间相互作用的网络(高复杂的,和其他的分子状态信息)。
虽然适应任何分子系统的结构和相互关系。
他是非常强大的,在于联合大的数据库(蛋白质,DNA,和对人类和生物日益重要的遗传)。
Cytoscape允许可视化的网络与文件,显型,其它分子状态信息,和链接网络到功能注释。
Cytoscape的重要组织方式是网络,因子,蛋白质和分子用点表示,两点间的交互关系用链接也就是边Cytoscape的发展Cytoscape软件是由以下的机构联合完成的:Institute for Systems Biology (Leroy Hood lab), theUniversity of California San Diego (Trey Ideker lab), Memorial Sloan-Kettering Cancer Center (ChrisSander lab), the Institut Pasteur (Benno Schwikowski lab), Agilent Technologies (Annette Adler lab) andthe University of California, San Francisco (Bruce Conklin lab).可以访问 得知详细情况许可Cytoscape是受the GNU LGPL (Lesser General Public License)保护的。
它是这个使用手册的附属品,但是可以在线/copyleft/lesser.txt.找到。
Cytoscape包括许多的开源库,详细的解释在这个使用手册/Acknowledgements 下。
Cytoscape2.6的新特点Cytoscape2.6包含了许多新的特色,增加改进软件的执行性和可用性。
这些新增功能包括: Web Service Client Manager frame work to integrate web service clients into Cytoscape.网络客户服务管理ٛ Web Service client plugins for downloading networks from Pathway Commons, IntAct, and NCBI EntrezGene.网络客户服务插件从路径命令。
IntAct 和NCBI EntrezGene下载ٛAnnotation import web service plugin for BioMart. This is mainly for ID translation/synonym mapping.注释进入BIoMart,这是一个主要的ID翻译/同义映射。
ٛ Cytoscape themes.Cytoscape 主题ٛ Dynamic filters.动态过滤ٛ Network Manager supports multiple network selection.网络管理支持多个网络的选择。
ٛ Label Positioning has been improved.标签位置的改进ٛ Session saving occurs in memory.节的保存记录ٛ XGMML Improvements.改良的XGMMLٛ Network loading improvements.改良的网络加载。
ٛ Linkout integrated with attribute browser .Linkout与属性浏览器整合。
ٛ Extra sample Visual Styles using new visual properties introduced in 2.5.新的可视化道具。
ٛ Many, many bug fixes!很多的嗅探器。
Cytoscape的安装首先要安装Java程序,才能够在Linux, Windows, and Mac OS X系统上运行。
虽然没有职位上的支持关系,其它的UNIX平台例如Solaris or FreeBSD需要高于Java 5以上的版本。
系统性能的要求Cytoscape的系统性能要求主要取决于它要处理的网络的大小、视图和操作。
小型网络的可视化大型网络的分析和可视化主频 1GHz 尽可能的快内存 512MB 2GB以上显卡 集成显卡 专业的显卡显示器 XGA(1024×768)宽或双安装过程第一步:安装Java程序Cytoscape 2.5 will no如果你的计算机没有安装,请下载Java SE 5 或 6.Cytoscape 2.5 不能再运行在低于Java version1.4x的版本下。
你必须安装Java SE 5或6。
一般说来,Java SE 6比5快。
如果你的机子兼容6系列,请应用 version 6。
第二步:安装Cytoscape软件Cytocape 的下载和安装有很多方案。
所有的方法都可以从 website.下载1、自动安装适合 Windows,Mac OS X和Linux 系统2、你可以通过压缩包安装3、你可以利用源代码建立Cytoscape4、你可以升级你的软件Cytoscape 安装(不包括平台)包括以下文件和目录文件 描述cytoscape.jar 主要的Cytoscape应用文档(Java 文档)cytoscape.sh 通过控制命令运行Cytoscape(Linux, Mac OS X)cytoscape.bat 手动运行Cytoscape(Wingdows)LICENSE.txt/html Cytoscape GNU LGPL 许可lib/ 库文件docs/ 不同版本的使用手册licenses/ Cytoscape不同库分布许可证plugins/ 在.jar格式中,目录包含插件sampleData/galFiltered.gml --样本分子交互网络文件galFiltered.sif –同样的网络在简单的交互格式galExpData.pvals –样本基因表达矩阵文件galFiltered.nodeAttrTable.xls –EXCEL格式的样本点属性文件galFiltered.cys –样本节文件BINDyeast.sif 在BIND 数据库中所有的蛋白质与蛋白质交互网络开始应用双击安装后的图标或者通过命令输入Cytoscape.sh (Linuxor Mac OS X))或双击cytoscape .bat(Windows)。
你可以经过.jar文件到Java直接利用命令java -Xmx512M -jar cytoscape.jar -p plugins。
-Xmx512M标记告诉Java分配更多的内存给Cytoscape和-p plugins选项告诉cytoscape直接导入所有的插件。
导入插件是很重要的因为很多关键的功能通过它导入Cytoscape 如:布局,过滤和属性浏览模块。
看命令栏章节了解更多细节。
在Windows系统中,可以直接双击.jar 文件导入。
当成功导入Cytoscape,可以看到如下窗口:内存的消耗说明用户导入大型的网络,Cytoscape需要内存的大小取决于网络点和边的数量和属性的数量。
下面有一些粗糙的内存分配意见:建议内存分配没有View点和边的总数建议内存大小0 - 70,000512M (default)70,000 - 150,000800M建议内存分配有View点和边的总数 建议内存大小0 - 20,000 512M (default)20,000 - 70,000 800M70,000 - 150,000 1G全部的内存给Cytoscape为了让Cytoscape最大的使用内存,你通过命令可以指定。
例如,你想分配1GB的内存,输入命令:java -Xmx1GB -jar cytoscape.jar -p plugins栈的大小分配还有一个选项涉及到内存。
在Cytoscape中的一些功能需用到大的栈空间(一些暂时的操作,如布局功能)这个值是独立于Xmx设置,有时候布局运算法则出错就是发生内存不够的原因。
为了避免出错,你可以设更大的尺寸利用-Xss命令。
如果布局大型网络失败,请尝试以下:java -Xmx1GB -Xss10M -jar cytoscape.jar -p plugins。
-Xss10M是设置栈的大小为10MB。
在大多数情况下,这就能解决空间不足的问题。
Cytoscape的界面当网络导入后,Cytoscape的界面如下:主窗口有以下几个成分组成:菜单栏在顶部(下面有其它菜单的详细信息)工具栏,包括普通功能的图标。
这些功能可通过菜单找到。
网络处理面板(顶部左边板块)。
它包含可选择整个网络的窗口(底部左边)网络主视图窗口,展示网络属性浏览板块(底部板块),展示选择的点或边的属性和能够修改属性值。
网络处理面板和属性浏览板块有使其独立的图标,于是被称为CytoPanels。
你可以点击CytoPanel右上角:如果你选择了这个控件,例如属性浏览板块,你就可以得到两个Cytoscape窗口,一个主窗口,一个新的CytoPanel2类似于下面所示的。
当你把鼠标移到单元上,就会弹出显示。
Cytoscape也右编辑功能,能让你创建和修改交互式网络通过画图和从主网络视图窗口的模板拉出点和边点的形状和边的箭头在模板中以定义为普通的可视风格。
编辑一个网络,就选择编辑标记CytoPanel 1。
编辑一个例子,模板包含CytoPanel 1和定义BioMoleculeEditor可视风格,展示如下。
菜单File(文件)File菜单包含很多基础文件功能:File-open(打开一个Cytoscape文件)File—New(建立一个新的网络,空的或已经存在的网络)File—Save(保存文件)File—Import(导入网络数据和属性)File—Export(输出数据和图)File—Print(打印图)File—Quit(关闭所有窗口退出程序)Edit(编辑)编辑菜单包含撤消(Undo)和重做(Redo)功能,这两命令影响属性浏览窗口,网络编辑窗口和布局窗口。