序列分析软件DNAMAN的使用方法共52页
- 格式:ppt
- 大小:4.08 MB
- 文档页数:52

序列分析软件DNAMAN 的使用方法简介DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN 5.2.9 Demo version 为例,简单介绍其使用方法。
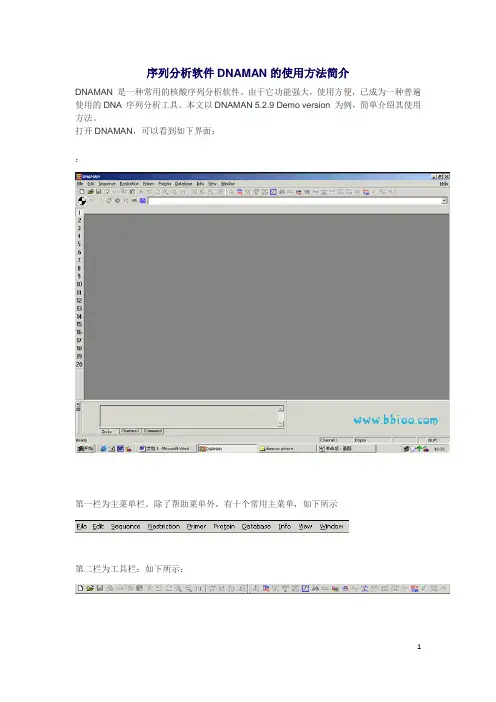
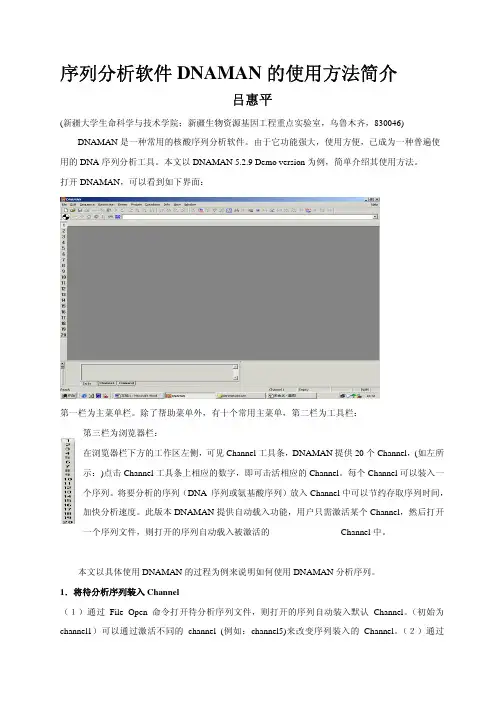
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为浏览器栏:在浏览器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,(如左所示:)点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的Channel 中。
本文以具体使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel(1)通过File Open 命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
(2)通过Sequence/Load Sequence 菜单的子菜单打开文件或将选定的部分序列装入Channel 。
通过Sequence/Current Sequence/Analysis Defination 命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence//Display Sequence 命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
对话框选项说明如下:Sequence &Composition 显示序列和成分Reverse Complement Sequence 显示待分析序列的反向互补序列Reverse Sequence 显示待分析序列的反向序列Complement Sequence 显示待分析序列的互补序列Double Stranded Sequence 显示待分析序列的双链序列RNA Sequence 显示待分析序列的对应RNA 序列3.DNA 序列的限制性酶切位点分析将待分析的序列装入Channel,点击要分析的Channel,然后通过Restriction/Analysis 命令打开对话框,如下所示:参数说明如下:Results 分析结果显示其中包括:Show summary(显示概要) Show sites on sequence(在结果中显示酶切位点)Draw restriction map(显示限制性酶切图)Draw restriction pattern(显示限制性酶切模式图)Ignore enzymes with more than(忽略大于某设定值的酶切位点)Ignore enzymes with less than(忽略小于某设定值的酶切位点)Target DNA (目标DNA 特性)circular(环型DNA),dam/dcm methylation(dam/dcm 甲基化)all DNA in Sequence Channel(选择此项,在Sequence Channel 中的所有序列将被分析,如果选择了Draw restriction pattern,那么当所有的channel 中共有两条DNA 时,则只能选择两个酶分析,如果共有三个以上DNA 时,则只能用一个酶分析。

序列分析软件DNAMAN 的使用方法简介DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN 5.2.9 Demo version 为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面::第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,如下所示第二栏为工具栏:如下所示:第三栏为浏览器栏:如下所示:在浏览器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,如左所示:点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel ,然后打开一个序列文件,则打开的序列自动载入被激活的Channel 中。
本文以具体使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel(1)通过File|Open 命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel(例如:channel5)来改变序列装入的Channel。
(2)通过Sequence|Load Sequence 菜单的子菜单打开文件或将选定的部分序列装入Channel。
可以通过Sequence|Current Sequence|Analysis Defination 命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence|Display Sequence 命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。


dnaman基因序列的比对方法
DNAMAN是用于多序列比对、PCR引物设计、限制性酶切分析、质粒绘图、蛋白质分析等的高度集成化的分子生物学综合应用软件。
以下是使用DNAMAN进行基因序列比对的步骤:
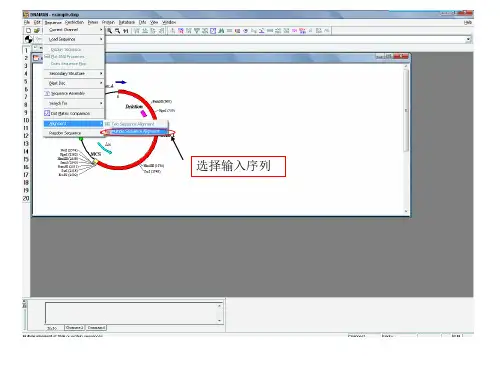
1. 打开DNAMAN,点击“Sequence-Alignment-Multiple sequence alignment”,进入比对页面。
2. 点击“File”,上传序列文件(fasta格式),选择序列类型,点击“Next”。
3. 这一步和下一步默认即可。
4. 参数默认即可,点击“Finish”,即可得到比对结果。
5. 若需要导出图,点击“Output-Graphic file”,保存EMF格式图片。
随后在画图工具中另存为需要的照片格式即可。
以上步骤仅供参考,建议查阅DNAMAN软件使用说明或咨询专业人士,
获取更准确的信息。

DNAMAN序列比对方法
1、序列导入:
打开DNAman软件,单击channel1以激活通道1,再单击file-open或者文件夹图标以浏览电脑文件,选择所有文件方可显示电脑中之前存储的fasta或txt格式的文件,选中要导入的文件后(注意导入通道内的序列是fasta格式的即带大于号形式的序列),再依次单击channel2、3、4……依次导入其他fasta格式的蛋白序列。
2、比对分析:
单击Sequence-Multiple sequence alignment,选择protein,单击channel,选择所有要比对的channel,OK后单击下一步,选择Fast alignment,单击下一步,选择默认的Quick alignment(如果前面没有选择Fast alignment,则这一步选择Dynamic alignment),单击完成。
3、设置Option
单击Options-Shading homology,在Shading type里设置相应颜色,单击确定。
另外,Options-Preference里选项可做调整,比如勾选No pos label in Printing/Output则不出现氨基酸的个数标示,比如不勾选Show consensus sequence,则不出现一致序列,这样既美观又有了更多的空间去标示motif等。
4、输出图片
单击Output-Graphic (EMF) File,即导出图片格式的比对文件。

序列比对的理论基础是进化学说:如果两个序列之间具有足够的相似性,就推测二者可能有共同的进化祖先,经过序列内残基的替换、残基或序列片段的缺失、以及序列重组等遗传变异过程分别演化而来。
序列相似和序列同源是不同的概念,序列之间的相似程度是可以量化的参数,而序列是否同源需要有进化事实的验证。
物以类聚人以群分,就像你要了解一个人可以通过了解他的朋友一样,序列比对是从已知获得未知的一个十分有用的方法。
另外,物种亲缘树的构建都需要进行生物分子序列的相似性比较。
序列比对按照数目、范围和对象来分,可以分为:o两序列比对和多序列比对o全局比对和局部比对o核酸序列比对和氨基酸序列比对。
限于篇幅,今天只给大家介绍如何使用DNAMAN 8作核酸多序列比对。
多序列比对就是把两条以上可能有系统进化关系的序列进行比对的方法。
其意义在于它能够把不同种属的相关序列的比对结果按照特定的格式输出,并且在一定程度上反映它们之间的相似性。
首先,在解螺旋回复0628下载DNAMAN 8软件。
打开后可以看到以下界面:第一栏为主菜单栏,除了帮助菜单外,有十个常用主菜单;第二栏为工具栏;第三栏为浏览器栏。
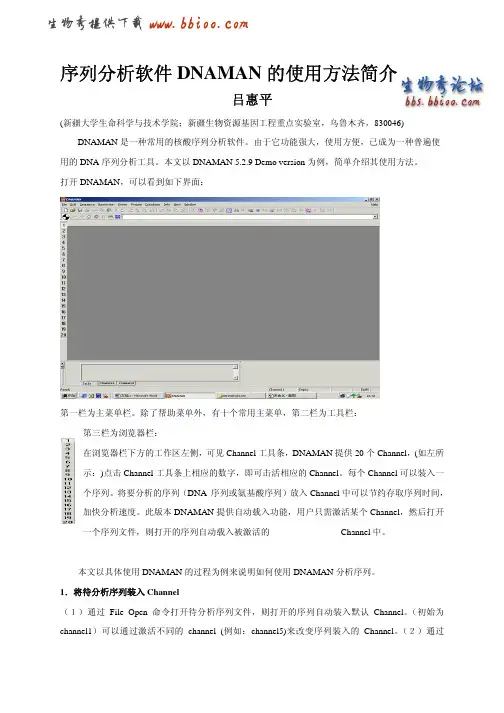
打开File-New,将序列粘贴到弹出的窗口中,点击File-save,保存到指定的文件夹。
将所需比对的序列保存好以后,选中Sequence—Aligment—Multiple aligment sequence 进行多序列比较。
在弹出的窗口Sequence&Files中加载序列,File、Fold、channel、Database分别表示从文件、文件夹、channel和数据库中获取序列。
勾选窗口中的“DNA”,点击“下一步”。
在弹出的窗口Method中,“optimalaligment”最佳比对方式中有四个高大上的选项:Full Alignment(完全比对)、Prosile Aligment(轮廓比对)、New Swquence on Profile (轮廓上的新序列)、Fast Alignment(快速比对),本文选择了Fast Alignment,并且勾选了Try both strands(尝试使用双链)。
序列分析软件DNAMAN的使用方法简介吕惠平(新疆大学生命科学与技术学院;新疆生物资源基因工程重点实验室,乌鲁木齐,830046) DNAMAN是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA序列分析工具。
本文以DNAMAN 5.2.9 Demo version为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为浏览器栏:在浏览器栏下方的工作区左侧,可见Channel工具条,DNAMAN提供20个Channel,(如左所示:)点击Channel工具条上相应的数字,即可击活相应的Channel。
每个Channel可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel中可以节约存取序列时间,加快分析速度。
此版本DNAMAN提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的 Channel中。
本文以具体使用DNAMAN的过程为例来说明如何使用DNAMAN分析序列。
1.将待分析序列装入Channel(1)通过File Open命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
(2)通过Sequence/Load Sequence菜单的子菜单打开文件或将选定的部分序列装入Channel。
通过Sequence/Current Sequence/Analysis Defination命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence//Display Sequence命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
序列分析软件DNAMAN的使用方法简介吕惠平(新疆大学生命科学与技术学院;新疆生物资源基因工程重点实验室,乌鲁木齐,830046) DNAMAN是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA序列分析工具。
本文以DNAMAN 5.2.9 Demo version为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为浏览器栏:在浏览器栏下方的工作区左侧,可见Channel工具条,DNAMAN提供20个Channel,(如左所示:)点击Channel工具条上相应的数字,即可击活相应的Channel。
每个Channel可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel中可以节约存取序列时间,加快分析速度。
此版本DNAMAN提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的 Channel中。
本文以具体使用DNAMAN的过程为例来说明如何使用DNAMAN分析序列。
1.将待分析序列装入Channel(1)通过File Open命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
(2)通过Sequence/Load Sequence菜单的子菜单打开文件或将选定的部分序列装入Channel。
通过Sequence/Current Sequence/Analysis Defination命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence//Display Sequence命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
DNAMAN的使用方法第五章 DNAMAN 的使用方法DNAMAN是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA序列分析工具。
本文以DNAMAN 5.2.9 Demo version为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,如下所示:第二栏为工具栏:如下所示:第三栏为浏览器栏:如下所示:在浏览器栏下方的工作区左侧,可见Channel工具条,DNAMAN提供20个Channel,如左所示:点击Channel工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel中可以节约存取序列时间,加快分析速度。
此版本DNAMAN提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的Channel中。
本文以具体使用DNAMAN的过程为例来说明如何使用DNAMAN分析序列。
1(将待分析序列装入Channel(,)通过File|Open命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为 channel1)可以通过激活不同的channel(例如:channel5)来改变序列默认装入的Channel。
(,)通过Sequence|Load Sequence菜单的子菜单打开文件或将选定的部分序列装入Channel。
如果只想分析序列的一部分,或者给待分析的序列添加批注,点击激活该序列所在的Channel,通过Sequence|Current Sequence|Analysis Defination命令打开一个对话框,如下所示:对话框选项说明如下:Name 序列名称Circular DNA 环形DNAStart pos 待分析序列起点End pos 待分析序列终点根据需要,可以设定上述选项的内容,如果要分析整个序列,可以点击按钮,如果当前序列不是DNA,则可点击按钮,如果要添加或修改批注,可以使用(添加),(移除),和(清除全部)三个按钮进行操作。
DNAMAN使用说明书DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN 5.2.9 Demo version 为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为浏览器栏:在浏览器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,(如左所示:)点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的Channel 中。
本文以具体使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel(1)通过File Open 命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
(2)通过Sequence/Load Sequence 菜单的子菜单打开文件或将选定的部分序列装入Channel 。
通过Sequence/Current Sequence/Analysis Defination 命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence//Display Sequence 命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
对话框选项说明如下:Sequence &Composition 显示序列和成分Reverse Complement Sequence 显示待分析序列的反向互补序列Reverse Sequence 显示待分析序列的反向序列Complement Sequence 显示待分析序列的互补序列Double Stranded Sequence 显示待分析序列的双链序列RNA Sequence 显示待分析序列的对应RNA 序列3.DNA 序列的限制性酶切位点分析将待分析的序列装入Channel,点击要分析的Channel,然后通过Restriction/Analysis 命令打开对话框,如下所示:参数说明如下:Results 分析结果显示其中包括:Show summary(显示概要) Show sites on sequence(在结果中显示酶切位点)Draw restriction map(显示限制性酶切图)Draw restriction pattern (显示限制性酶切模式图)Ignore enzymes with more than(忽略大于某设定值的酶切位点)Ignore enzymes with less than(忽略小于某设定值的酶切位点)Target DNA (目标DNA 特性)circular(环型DNA),dam/dcm methylation(dam/dcm 甲基化)all DNA in Sequence Channel(选择此项,在Sequence Channel 中的所有序列将被分析,如果选择了Draw restriction pattern,那么当所有的channel 中共有两条DNA 时,则只能选择两个酶分析,如果共有三个以上DNA 时,则只能用一个酶分析。
序列分析软件DNAMAN的使用方法简介DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN 5.2.9 Demo version 为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面::第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,如下所示第二栏为工具栏:如下所示:第三栏为浏览器栏:如下所示:在浏览器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,如左所示:点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel ,然后打开一个序列文件,则打开的序列自动载入被激活的Channel 中。
本文以具体使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel(1)通过File|Open 命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel(例如:channel5)来改变序列装入的Channel。
(2)通过Sequence|Load Sequence 菜单的子菜单打开文件或将选定的部分序列装入Channel。
可以通过Sequence|Current Sequence|Analysis Defination 命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence|Display Sequence 命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
DNAMAN使用说明书DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN Demo version 为例,简单介绍其使用方法。
翻开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为阅读器栏:在阅读器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,(如左所示:)点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列〔DNA 序列或氨基酸序列〕放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel,然后翻开一个序列文件,那么翻开的序列自动载入被激活的Channel 中。
本文以详细使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel〔1〕通过File Open 命令翻开待分析序列文件,那么翻开的序列自动装入默认Channel。
〔初始为channel1〕可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
〔2〕通过Sequence/Load Sequence 菜单的子菜单翻开文件或将选定的局部序列装入Channel 。
通过Sequence/Current Sequence/Analysis Defination 命令翻开一个对话框,通过此对话框可以设定序列的性质〔DNA 或蛋白质〕,名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence择需要的选项,点击按钮,出现:点击按钮,完成操作。
7.画质粒形式图我们常常要用到各种质粒图,无论是制作幻灯片,还是发表文章,常常需要质粒图。
DNAMAN提供强大的绘质粒图功能,能满足我们的需要。