找一个基因的启动子
- 格式:doc
- 大小:476.00 KB
- 文档页数:8

如何找一个基因的启动子序列呢一个基因的启动子序列是一个基因组区域,位于基因的上游,并能够识别和结合转录因子,调控基因的转录活性。
寻找一个基因的启动子序列可以通过多种方法和技术来进行。
1. 基因组数据挖掘:最简单的方法是使用公开的基因组数据库,例如Ensembl、NCBI等,使用基因名或序列信息目标基因,并获取其序列信息。
这些数据库通常会提供基因的起始位置和上游区域的信息。
2.序列比对和多序列比较:如果基因组数据库中没有目标基因的启动子序列信息,可以通过对已知相关物种的基因组进行序列比对来获取启动子序列。
过去研究或其他相关文献中可能已经报道了该基因位点的启动子信息,可以通过多序列比较来找到高度保守的区域进行分析。
3.实验方法:寻找基因的启动子序列也可以通过实验方法来进行。
以下是几个常用的实验方法:-基因克隆:通过PCR扩增目标基因的上游区域,然后将PCR产物克隆到适当的载体中进行测序。
从测序结果中截取相应的序列作为启动子序列。
- 5' RACE(Rapid Amplification of cDNA Ends):通过5' RACE技术,可以找到目标基因的转录起始位点,从而确定启动子序列。
这种方法从mRNA上游端引导逆转录聚合酶链式反应(RT-PCR),然后再通过测序获取启动子序列。
-转录组学方法:RNA测序和转录组学方法可以检测到基因的转录产物,从而很大程度上能够帮助确定启动子序列。
RNA测序可以生成从基因的5'端到3'端的转录产物的序列信息,因此可以利用这些数据来识别基因的启动子区域。
4. 计算方法:计算方法可以利用一些生物学特征或机器学习算法来预测基因的启动子序列。
例如,启动子序列通常富含一些特定的DNA序列模式,如TATA box、CAAT box和GC box等。
利用这些DNA序列模式的分布和相互作用关系,可以预测和确定基因的启动子区域。
在寻找基因的启动子序列时,需要根据研究目的选择适当的方法。
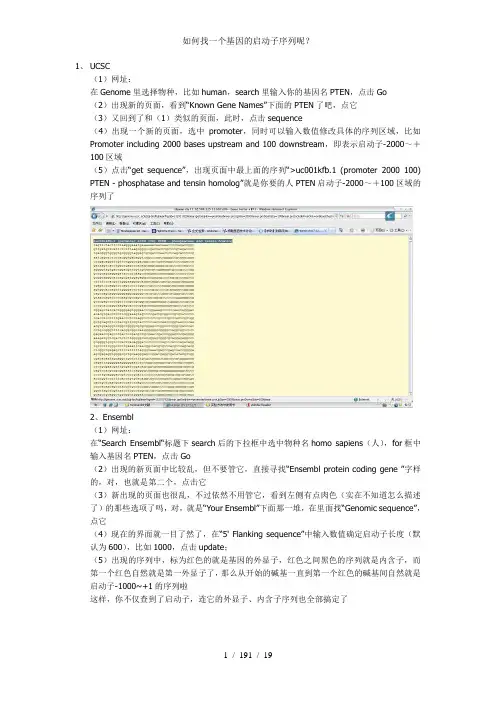
1、UCSC(1)网址:在Genome里选择物种,比如human,search里输入你的基因名PTEN,点击Go(2)出现新的页面,看到“Known Gene Names”下面的PTEN了吧,点它(3)又回到了和(1)类似的页面,此时,点击sequence(4)出现一个新的页面,选中promoter,同时可以输入数值修改具体的序列区域,比如Promoter including 2000 bases upstream and 100 downstream,即表示启动子-2000~+100区域(5)点击“get sequence”,出现页面中最上面的序列“>uc001kfb.1 (promoter 2000 100) PTEN - phosphatase and tensin homolog”就是你要的人PTEN启动子-2000~+100区域的序列了2、Ensembl(1)网址:在“Search Ensembl“标题下search后的下拉框中选中物种名homo sapiens(人),for框中输入基因名PTEN,点击Go(2)出现的新页面中比较乱,但不要管它,直接寻找“Ensembl protein coding gene ”字样的,对,也就是第二个,点击它(3)新出现的页面也很乱,不过依然不用管它,看到左侧有点肉色(实在不知道怎么描述了)的那些选项了吗,对,就是“Your Ensembl”下面那一堆,在里面找“Genomic sequence”,点它(4)现在的界面就一目了然了,在“5' Flanking sequence”中输入数值确定启动子长度(默认为600),比如1000,点击update;(5)出现的序列中,标为红色的就是基因的外显子,红色之间黑色的序列就是内含子,而第一个红色自然就是第一外显子了,那么从开始的碱基一直到第一个红色的碱基间自然就是启动子-1000~+1的序列啦这样,你不仅查到了启动子,连它的外显子、内含子序列也全部搞定了3、SIB-EPD(1)网址:(2)具体使用方法大同小异,就是输入物种名、基因名,限定启动子序列区域不过有了前两个,我想已经足够用了,个人感觉SIB-EPD的库容量太小,很多基因查不到我以前回的贴,总结一下ensembl一般也和NCBI的一致,你的情况可能例外。

如何查找一个基因的启动子序列发表者:刘小丰 (访问人次:6102)刘小丰收集整理定义:启动子是参与特定基因转录及其调控的DNA序列。
包含核心启动子区域和调控区域。
核心启动子区域产生基础水平的转录,调控区域能够对不同的环境条件作出应答,对基因的表达水平做出相应的调节。
区域:启动子的范围非常大,可以包含转录起始位点上游2000bp,有些特定基因的转录区内部也存在着转录因子的结合位点,因此也属于启动子范围。
这项搜寻要从UCSC基因组浏览器开始,网址为/cgi-bin/hgGateway。
以编码pendrin (PDS)的基因为例来说明上述问题。
PDS与耳蜗的异常发育、感觉神经性听力下降以及弥散性甲状腺增大(甲状腺肿)有关。
进入UCSC的主页后,在Organism的下拉菜单中选择Human,然后点击Browser。
使用者现在到了人类基因组浏览器入口。
本例的搜寻很简单:在assembly的下拉菜单中选择Dec. 2001,在position框中键入pendrin,然后点击Submit。
返回的页面结果显示一个已知的基因和两个mRNA序列。
继续点击mRNA序列的登录号AF030880,出现包含这个mRNA区域的图解概要。
为了获得这个区域更清晰的图像,点击紧靠zoom out的1.5X按钮。
最后点击页面中部的reset all按钮,使各个路径的设置恢复默认状态。
然而,对于本例的搜寻目的来说,默认设置不是理想的设置。
按照视图利用页面底部的Track Controls按纽,将一些路径设置为hide模式(即不显示),其他设置为dense模式(所有资料密集在一条直线上);另一些路径设置为full模式(每个特征有一个分开的线条,最多达300)。
在考虑这些路径内究竟存在那些资料之前,对这些路径的内容和表现做一个简要的讨论是必要的,许多这些讨论是由外界提供给UCSC的。
下面是对基因预测方法的更进一步讨论,这些信息也可以在其他地方找到。

定义:启动子是参与特定基因转录及其调控的DNA序列。
包含核心启动子区域和调控区域。
核心启动子区域产生基础水平的转录,调控区域能够对不同的环境条件作出应答,对基因的表达水平做出相应的调节。
一般查阅外文文献,老外从转录起始位点(Transcription Strart Site,TSS,记为+1位)开始上溯2K -3K的区间算做是启动子区域:启动子的范围非常大,可以包含转录起始位点上游2000bp,有些特定基因的转录区内部也存在着转录因子的结合位点,因此也属于启动子范围。
票数Do One Thing, And Do It Well. mybbff edited on 2005-07-22 08:41••••2005-05-07 11:23 分享分享到哪里?•••••••••下面以BCL-2基因为例,查找查找该基因的启动子区域,首先要找到该基因的基因组序列。
去NCBI吧,在Search的下拉菜单里找到Gene,在检索项里输入Bcl-2,检索第一项就是bcl-2 for human,点进去看看啥样。
票数Do One Thing, And Do It Well.•••••2005-05-07 11:29 分享分享到哪里?••••••首先你可以看到该基因的参考序列(reference sequence),然后看到bcl-2的位置和基因组背景。
bcl-2上游是PHLPP,下游是FVT1基因。
在这个长长的网页的最后是已经注册的Bcl-2基因的信息。
票数Do One Thing, And Do It Well. Revelation edited on 2005-05-07 11:59 ••2005-05-07 11:35 分享分享到哪里?••••••••看到基因组序列了么,点进去,根据序列信息自己就能定位转录起始位点,上游就是promoter了,简单吧。
不!我觉得麻烦。
有更简单的方法么?有!注意到在网页的开头有这么个链接么?HGNC:990票数Do One Thing, And Do It Well.••2005-05-07 11:38 分享•••分享到哪里?••••••点进去,看看吧。

定义:启动子是参与特定基因转录及其调控的DNA序列。
包含核心启动子区域和调控区域。
核心启动子区域产生基础水平的转录,调控区域能够对不同的环境条件作出应答,对基因的表达水平做出相应的调节。
区域:启动子的范围非常大,可以包含转录起始位点上游2000bp,有些特定基因的转录区内部也存在着转录因子的结合位点,因此也属于启动子范围。
8票票数Do One Thing, And Do It Well. mybbff edited on 2005-07-22 08:41 举报∙超级细菌耐药性基因多重PCR检测∙【原创】ensembl 改版后如何查找启动子∙【原创】使用UCSC查找一个基因的启动子序列(终)∙【共享】如何查找基因启动子,外显子,内含子序列-最新的资料Revelation 2005-05-07 11:23 消息引用收藏分享分享到哪里?∙复制网址∙新浪微博∙34积分∙12得票∙246丁当加关注∙豆瓣社区∙腾讯微博∙开心网∙人人网下面以BCL-2基因为例,查找查找该基因的启动子区域,首先要找到该基因的基因组序列。
去NCBI吧,在Search的下拉菜单里找到Gene,在检索项里输入Bcl-2,检索第一项就是bcl-2 for human,点进去看看啥样。
0票票数Do One Thing, And Do It Well. 举报∙• 【消息】ACEI + ARB,你给血透患者用这样的组合吗?Revelation∙34积分∙12得票∙246丁当加关注2005-05-07 11:29 消息引用收藏分享分享到哪里?∙复制网址∙新浪微博∙豆瓣社区∙腾讯微博∙开心网∙人人网首先你可以看到该基因的参考序列(reference sequence),然后看到bcl-2的位置和基因组背景。
bcl-2上游是PHLPP,下游是FVT1基因。
在这个长长的网页的最后是已经注册的Bcl-2基因的信息。
0票票数Do One Thing, And Do It Well. Revelation edited on 2005-05-07 11:59 举报∙基因过表达Revelation 2005-05-07 11:35 消息引用收藏分享分享到哪里?∙复制网址∙新浪微博∙34积分∙12得票∙246丁当加关注∙豆瓣社区∙腾讯微博∙开心网∙人人网看到基因组序列了么,点进去,根据序列信息自己就能定位转录起始位点,上游就是promoter了,简单吧。
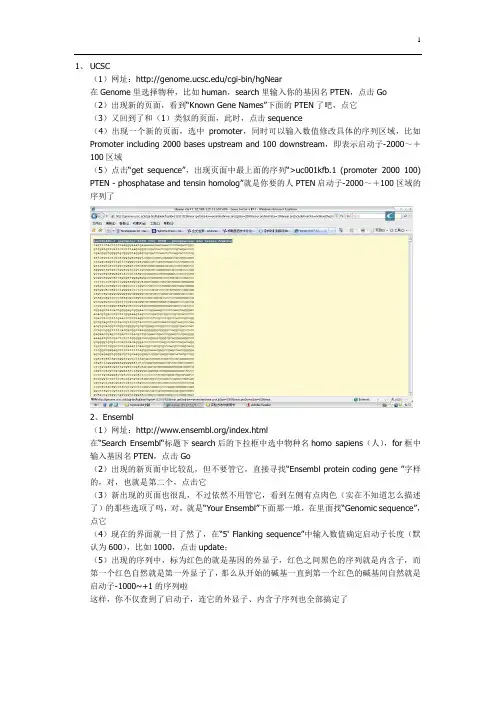
1、UCSC(1)网址:/cgi-bin/hgNear在Genome里选择物种,比如human,search里输入你的基因名PTEN,点击Go(2)出现新的页面,看到“Known Gene Names”下面的PTEN了吧,点它(3)又回到了和(1)类似的页面,此时,点击sequence(4)出现一个新的页面,选中promoter,同时可以输入数值修改具体的序列区域,比如Promoter including 2000 bases upstream and 100 downstream,即表示启动子-2000~+100区域(5)点击“get sequence”,出现页面中最上面的序列“>uc001kfb.1 (promoter 2000 100) PTEN - phosphatase and tensin homolog”就是你要的人PTEN启动子-2000~+100区域的序列了2、Ensembl(1)网址:/index.html在“Search Ensembl“标题下search后的下拉框中选中物种名homo sapiens(人),for框中输入基因名PTEN,点击Go(2)出现的新页面中比较乱,但不要管它,直接寻找“Ensembl protein coding gene ”字样的,对,也就是第二个,点击它(3)新出现的页面也很乱,不过依然不用管它,看到左侧有点肉色(实在不知道怎么描述了)的那些选项了吗,对,就是“Your Ensembl”下面那一堆,在里面找“Genomic sequence”,点它(4)现在的界面就一目了然了,在“5' Flanking sequence”中输入数值确定启动子长度(默认为600),比如1000,点击update;(5)出现的序列中,标为红色的就是基因的外显子,红色之间黑色的序列就是内含子,而第一个红色自然就是第一外显子了,那么从开始的碱基一直到第一个红色的碱基间自然就是启动子-1000~+1的序列啦这样,你不仅查到了启动子,连它的外显子、内含子序列也全部搞定了3、SIB-EPD(1)网址:http://www.epd.isb-sib.ch/(2)具体使用方法大同小异,就是输入物种名、基因名,限定启动子序列区域不过有了前两个,我想已经足够用了,个人感觉SIB-EPD的库容量太小,很多基因查不到我以前回的贴,总结一下ensembl一般也和NCBI的一致,你的情况可能例外。

定义:启动子是参与特定基因转录及其调控的DNA序列。
包含核心启动子区域和调控区域。
核心启动子区域产生基础水平的转录,调控区域能够对不同的环境条件作出应答,对基因的表达水平做出相应的调节。
区域:启动子的范围非常大,可以包含转录起始位点上游2000bp,有些特定基因的转录区内部也存在着转录因子的结合位点,因此也属于启动子范围。
8票票数Do One Thing, And Do It Well. mybbff edited on 2005-07-22 08:41 举报∙超级细菌耐药性基因多重PCR检测∙【原创】ensembl 改版后如何查找启动子∙【原创】使用UCSC查找一个基因的启动子序列(终)∙【共享】如何查找基因启动子,外显子,内含子序列-最新的资料Revelation 2005-05-07 11:23 消息引用收藏分享分享到哪里?∙复制网址∙新浪微博∙34积分∙12得票∙246丁当加关注∙豆瓣社区∙腾讯微博∙开心网∙人人网下面以BCL-2基因为例,查找查找该基因的启动子区域,首先要找到该基因的基因组序列。
去NCBI吧,在Search的下拉菜单里找到Gene,在检索项里输入Bcl-2,检索第一项就是bcl-2 for human,点进去看看啥样。
0票票数Do One Thing, And Do It Well. 举报∙• 【消息】ACEI + ARB,你给血透患者用这样的组合吗?Revelation∙34积分∙12得票∙246丁当加关注2005-05-07 11:29 消息引用收藏分享分享到哪里?∙复制网址∙新浪微博∙豆瓣社区∙腾讯微博∙开心网∙人人网首先你可以看到该基因的参考序列(reference sequence),然后看到bcl-2的位置和基因组背景。
bcl-2上游是PHLPP,下游是FVT1基因。
在这个长长的网页的最后是已经注册的Bcl-2基因的信息。
0票票数Do One Thing, And Do It Well. Revelation edited on 2005-05-07 11:59 举报∙基因过表达Revelation 2005-05-07 11:35 消息引用收藏分享分享到哪里?∙复制网址∙新浪微博∙34积分∙12得票∙246丁当加关注∙豆瓣社区∙腾讯微博∙开心网∙人人网看到基因组序列了么,点进去,根据序列信息自己就能定位转录起始位点,上游就是promoter了,简单吧。

如何查找一个基因的启动子序列发表者:刘小丰 (访问人次:6102)刘小丰收集整理定义:启动子是参与特定基因转录及其调控的DNA序列。
包含核心启动子区域和调控区域。
核心启动子区域产生基础水平的转录,调控区域能够对不同的环境条件作出应答,对基因的表达水平做出相应的调节。
区域:启动子的范围非常大,可以包含转录起始位点上游2000bp,有些特定基因的转录区内部也存在着转录因子的结合位点,因此也属于启动子范围。
这项搜寻要从UCSC基因组浏览器开始,网址为/cgi-bin/hgGateway。
以编码pendrin (PDS)的基因为例来说明上述问题。
PDS与耳蜗的异常发育、感觉神经性听力下降以及弥散性甲状腺增大(甲状腺肿)有关。
进入UCSC的主页后,在Organism的下拉菜单中选择Human,然后点击Browser。
使用者现在到了人类基因组浏览器入口。
本例的搜寻很简单:在assembly的下拉菜单中选择Dec. 2001,在position框中键入pendrin,然后点击Submit。
返回的页面结果显示一个已知的基因和两个mRNA序列。
继续点击mRNA序列的登录号AF030880,出现包含这个mRNA区域的图解概要。
为了获得这个区域更清晰的图像,点击紧靠zoom out的1.5X按钮。
最后点击页面中部的reset all按钮,使各个路径的设置恢复默认状态。
然而,对于本例的搜寻目的来说,默认设置不是理想的设置。
按照视图利用页面底部的Track Controls按纽,将一些路径设置为hide模式(即不显示),其他设置为dense模式(所有资料密集在一条直线上);另一些路径设置为full模式(每个特征有一个分开的线条,最多达300)。
在考虑这些路径内究竟存在那些资料之前,对这些路径的内容和表现做一个简要的讨论是必要的,许多这些讨论是由外界提供给UCSC的。
下面是对基因预测方法的更进一步讨论,这些信息也可以在其他地方找到。

如何查找一个基因的启动子序列关键词:基因启动子序列软件定义:启动子是参与特定基因转录及其调控的DNA序列。
包含核心启动子区域和调控区域。
核心启动子区域产生基础水平的转录,调控区域能够对不同的环境条件作出应答,对基因的表达水平做出相应的调节。
区域:启动子的范围非常大,可以包含转录起始位点上游2000bp,有些特定基因的转录区内部也存在着转录因子的结合位点,因此也属于启动子范围。
这项搜寻要从UCSC基因组浏览器开始,网址为/。
以编码pendrin (PDS)的基因为例来说明上述问题。
PDS与耳蜗的异常发育、感觉神经性听力下降以及弥散性甲状腺增大(甲状腺肿)有关。
进入UCSC的主页后,在Organism的下拉菜单中选择Human,然后点击Browser。
使用者现在到了人类基因组浏览器入口。
本例的搜寻很简单:在assembly的下拉菜单中选择Dec. 2001,在position框中键入pendrin,然后点击Submit。
返回的页面结果显示一个已知的基因和两个mRNA序列。
继续点击mRNA序列的登录号AF030880,出现包含这个mRNA区域的图解概要。
为了获得这个区域更清晰的图像,点击紧靠zoom out的1.5X按钮。
最后点击页面中部的reset all按钮,使各个路径的设置恢复默认状态。
然而,对于本例的搜寻目的来说,默认设置不是理想的设置。
按照视图利用页面底部的Track Controls按纽,将一些路径设置为hide模式(即不显示),其他设置为dense模式(所有资料密集在一条直线上);另一些路径设置为full 模式(每个特征有一个分开的线条,最多达300)。
在考虑这些路径内究竟存在那些资料之前,对这些路径的内容和表现做一个简要的讨论是必要的,许多这些讨论是由外界提供给UCSC的。
下面是对基因预测方法的更进一步讨论,这些信息也可以在其他地方找到。
对于Known Genes(已知基因)和预测的基因路径来说,一般的惯例是以一个高的垂直线或块状表示每个编码外显子,以短的垂直线或块状表示5′端和3′端非翻译区。

如何查找一个基因的启动子序列定义:启动子是参与特定基因转录及其调控的DNA序列。
包含核心启动子区域和调控区域。
核心启动子区域产生基础水平的转录,调控区域能够对不同的环境条件作出应答,对基因的表达水平做出相应的调节。
区域:启动子的范围非常大,可以包含转录起始位点上游2000bp,有些特定基因的转录区内部也存在着转录因子的结合位点,因此也属于启动子范围。
这项搜寻要从UCSC基因组浏览器开始,网址为/。
以编码pendrin (PDS)的基因为例来说明上述问题。
PDS与耳蜗的异常发育、感觉神经性听力下降以及弥散性甲状腺增大(甲状腺肿)有关。
进入UCSC的主页后,在Organism的下拉菜单中选择Human,然后点击Browser。
使用者现在到了人类基因组浏览器入口。
本例的搜寻很简单:在assembly的下拉菜单中选择Dec. 2001,在position 框中键入pendrin,然后点击Submit。
返回的页面结果显示一个已知的基因和两个mRNA序列。
继续点击mRNA序列的登录号AF030880,出现包含这个mRNA区域的图解概要。
为了获得这个区域更清晰的图像,点击紧靠zoom out的1.5X按钮。
最后点击页面中部的reset all按钮,使各个路径的设置恢复默认状态。
然而,对于本例的搜寻目的来说,默认设置不是理想的设置。
按照视图利用页面底部的Track Controls 按纽,将一些路径设置为hide模式(即不显示),其他设置为dense模式(所有资料密集在一条直线上);另一些路径设置为full模式(每个特征有一个分开的线条,最多达300)。
在考虑这些路径内究竟存在那些资料之前,对这些路径的内容和表现做一个简要的讨论是必要的,许多这些讨论是由外界提供给UCSC 的。
下面是对基因预测方法的更进一步讨论,这些信息也可以在其他地方找到。
对于Known Genes(已知基因)和预测的基因路径来说,一般的惯例是以一个高的垂直线或块状表示每个编码外显子,以短的垂直线或块状表示5′端和3′端非翻译区。

如何查找一个基因的启动子序列如何查找一个基因的启动子序列定义:启动子是参与特定基因转录及其调控的DNA序列。
包含核心启动子区域和调控区域。
核心启动子区域产生基础水平的转录,调控区域能够对不同的环境条件作出应答,对基因的表达水平做出相应的调节。
区域:启动子的范围非常大,可以包含转录起始位点上游2000bp,有些特定基因的转录区内部也存在着转录因子的结合位点,因此也属于启动子范围。
南京妇幼保健院乳腺科刘小丰这项搜寻要从UCSC基因组浏览器开始,网址为/cgi-bin/hgGateway。
以编码pendrin (PDS)的基因为例来说明上述问题。
PDS与耳蜗的异常发育、感觉神经性听力下降以及弥散性甲状腺增大(甲状腺肿)有关。
进入UCSC的主页后,在Organism的下拉菜单中选择Human,然后点击Browser。
使用者现在到了人类基因组浏览器入口。
本例的搜寻很简单:在assembly的下拉菜单中选择Dec. 2001,在position框中键入pendrin,然后点击Submit。
返回的页面结果显示一个已知的基因和两个mRNA序列。
继续点击mRNA序列的登录号AF030880,出现包含这个mRNA区域的图解概要。
为了获得这个区域更清晰的图像,点击紧靠zoom out的1.5X按钮。
最后点击页面中部的reset all按钮,使各个路径的设置恢复默认状态。
然而,对于本例的搜寻目的来说,默认设置不是理想的设置。
按照视图利用页面底部的Track Controls按纽,将一些路径设置为hide模式(即不显示),其他设置为dense模式(所有资料密集在一条直线上);另一些路径设置为full模式(每个特征有一个分开的线条,最多达300)。
在考虑这些路径内究竟存在那些资料之前,对这些路径的内容和表现做一个简要的讨论是必要的,许多这些讨论是由外界提供给UCSC的。
下面是对基因预测方法的更进一步讨论,这些信息也可以在其他地方找到。
如何查找基因的启动子区基因的启动子区是基因的调控区域,其位于基因的上游区域。
启动子区域的特点是具有包括启动子、增强子、转录因子结合位点等在内的一系列调控元件,这些元件共同参与了基因的转录调控。
找到一个基因的启动子区,可以帮助我们理解基因的调控机制,进而揭示基因功能和可能的突变带来的影响。
下面将介绍几种常用的方法来查找基因的启动子区。
1.基于生物信息学的预测方法:在基因组学研究中,有很多基于生物信息学的预测方法可以用来查找启动子区域。
这些方法的基本原理是通过分析DNA序列中的一些保守模体和序列特征来预测潜在的启动子区域。
常用的生物信息学工具有TSSGuru、PromoterInspector、Softberry和PromoterScan等,这些工具常常依赖于一些已知的和保守的启动子模体来进行预测。
2.实验室方法:实验室方法一般用于鉴定启动子区域的转录起始位点(TSS)。
这些方法包括实验室测定的转录起始位点显示法(5'-RACE)和转录起始位点定位法(TSS mapping)。
5'-RACE利用了RNA反转录和PCR扩增的原理,可以将对应于转录起始位点的RNA序列扩增出来,并通过测序鉴定转录起始位点。
TSS mapping是一种高通量测定转录起始位点的方法,它可以通过酶切或测序技术鉴定转录起始位点。
3.基于转录因子结合的方法:转录因子是调控基因表达的关键分子,它们结合到基因的启动子区域上,并激活或抑制基因的转录。
通过研究转录因子的结合位点可以找到潜在的启动子区域。
常用的方法有DNA亲和层析法(DNA affinitychromatography)、ChIP-Seq和DNase-seq等。
其中,ChIP-Seq是一种高通量的方法,可以通过将转录因子与其结合DNA片段一起进行测序,从而确定转录因子结合位点和相关启动子区域。
4.跨物种比较法:在物种间比较的基础上查找启动子区域是一种常用的方法。
如何查找一个基因的启动子序列- UCSC GenomeBioinformatics Site来源:shumingky 发布时间:2009-09-13 查看次数:1712本篇文章写于早期,随着UCSC网站的改版,本文部分内容与网站不一致,读者操作起来可能不方便。
为此,站长原创了一篇文章:“应用UCSC/Ensembl查找基因启动子(promoter)、内含子、外显子序列”,大家可按该文章讲述的方法进行查询基因的启动子,这篇文章之所以没删除,原因是其中有些原理性的内容是一致的,读者可将这两篇文章结合起来阅读。
关键词:基因,启动子序列,软件定义:启动子是参与特定基因转录及其调控的DNA序列。
包含核心启动子区域和调控区域。
核心启动子区域产生基础水平的转录,调控区域能够对不同的环境条件作出应答,对基因的表达水平做出相应的调节。
区域:启动子的范围非常大,可以包含转录起始位点上游2000bp,有些特定基因的转录区内部也存在着转录因子的结合位点,因此也属于启动子范围。
这项搜寻要从UCSC基因组浏览器开始,网址为/。
以编码pendrin (PDS)的基因为例来说明上述问题。
PDS与耳蜗的异常发育、感觉神经性听力下降以及弥散性甲状腺增大(甲状腺肿)有关。
进入UCSC的主页后,在Organism的下拉菜单中选择Human,然后点击B rowser。
使用者现在到了人类基因组浏览器入口。
本例的搜寻很简单:在assemb ly的下拉菜单中选择Dec. 2001,在position框中键入pendrin,然后点击Submi t。
返回的页面结果显示一个已知的基因和两个mRNA序列。
继续点击mRNA序列的登录号AF030880,出现包含这个mRNA区域的图解概要。
为了获得这个区域更清晰的图像,点击紧靠zoom out的1.5X按钮。
最后点击页面中部的reset all按钮,使各个路径的设置恢复默认状态。
然而,对于本例的搜寻目的来说,默认设置不是理想的设置。
已知基因找启动子转录因子
在基因表达调控中,启动子转录因子起着至关重要的作用。
它
们是一类能够结合到基因启动子区域的蛋白质,能够调节基因的转
录过程,从而影响基因的表达。
因此,对于已知的基因,找到其对
应的启动子转录因子是非常重要的。
首先,要找到一个基因的启动子转录因子,需要对该基因的启
动子区域进行分析。
启动子区域通常位于基因的上游区域,包含一
系列的特定序列,如TATA盒、CAAT盒等。
这些序列是启动子转录
因子结合的位点,通过结合这些序列,启动子转录因子能够调节基
因的转录。
一种常用的方法是通过生物信息学分析,寻找基因的启动子区域,并预测可能结合的转录因子。
这可以通过在基因组数据库中搜
索基因的启动子序列,并使用启动子预测软件来预测可能结合的转
录因子。
此外,也可以利用已知的启动子转录因子的结合序列信息,对基因的启动子序列进行比对,找到可能的结合位点。
另一种方法是利用实验手段,如染色质免疫沉淀(ChIP)技术,通过将细胞中的蛋白质与DNA交联,然后利用特定的抗体沉淀出启
动子转录因子结合的DNA片段,最后通过测序分析确定启动子转录因子的结合位点。
一旦找到了基因的启动子转录因子,就可以进一步研究其调控机制,以及在疾病发生和发展中的作用。
此外,对启动子转录因子的研究也为基因治疗和药物开发提供了重要的信息。
总之,已知基因找启动子转录因子是基因表达调控研究中的重要一环,它有助于我们深入理解基因的调控机制,为疾病的治疗和药物的开发提供重要的参考。
因此,对于基因的启动子转录因子的研究具有重要的科学意义和应用价值。
1、UCSC(1)网址:/cgi-bin/hgNear在Genome里选择物种,比如human,search里输入你的基因名PTEN,点击Go(2)出现新的页面,看到“Known Gene Names”下面的PTEN了吧,点它(3)又回到了和(1)类似的页面,此时,点击sequence(4)出现一个新的页面,选中promoter,同时可以输入数值修改具体的序列区域,比如Promoter including 2000 bases upstream and 100 downstream,即表示启动子-2000~+100区域(5)点击“get sequence”,出现页面中最上面的序列“>uc001kfb.1 (promoter 2000 100) PTEN - phosphatase and tensin homolog”就是你要的人PTEN启动子-2000~+100区域的序列了2、Ensembl(1)网址:/index.html在“Search Ensembl“标题下search后的下拉框中选中物种名homo sapiens(人),for框中输入基因名PTEN,点击Go(2)出现的新页面中比较乱,但不要管它,直接寻找“Ensembl protein coding gene ”字样的,对,也就是第二个,点击它(3)新出现的页面也很乱,不过依然不用管它,看到左侧有点肉色(实在不知道怎么描述了)的那些选项了吗,对,就是“Your Ensembl”下面那一堆,在里面找“Genomic sequence”,点它(4)现在的界面就一目了然了,在“5' Flanking sequence”中输入数值确定启动子长度(默认为600),比如1000,点击update;(5)出现的序列中,标为红色的就是基因的外显子,红色之间黑色的序列就是内含子,而第一个红色自然就是第一外显子了,那么从开始的碱基一直到第一个红色的碱基间自然就是启动子-1000~+1的序列啦这样,你不仅查到了启动子,连它的外显子、内含子序列也全部搞定了3、SIB-EPD(1)网址:http://www.epd.isb-sib.ch/(2)具体使用方法大同小异,就是输入物种名、基因名,限定启动子序列区域不过有了前两个,我想已经足够用了,个人感觉SIB-EPD的库容量太小,很多基因查不到我以前回的贴,总结一下ensembl一般也和NCBI的一致,你的情况可能例外。
1、UCSC
(1)网址:/cgi-bin/hgNear
在Genome里选择物种,比如human,search里输入你的基因名PTEN,点击Go
(2)出现新的页面,看到“Known Gene Names”下面的PTEN了吧,点它
(3)又回到了和(1)类似的页面,此时,点击sequence
(4)出现一个新的页面,选中promoter,同时可以输入数值修改具体的序列区域,比如Promoter including 2000 bases upstream and 100 downstream,即表示启动子-2000~+100区域
(5)点击“get sequence”,出现页面中最上面的序列“>uc001kfb.1 (promoter 2000 100) PTEN - phosphatase and tensin homolog”就是你要的人PTEN启动子-2000~+100区域的序列了
2、Ensembl
(1)网址:/index.html
在“Search Ensembl“标题下search后的下拉框中选中物种名homo sapiens(人),for框中输入基因名PTEN,点击Go
(2)出现的新页面中比较乱,但不要管它,直接寻找“Ensembl protein coding gene ”字样的,对,也就是第二个,点击它
(3)新出现的页面也很乱,不过依然不用管它,看到左侧有点肉色(实在不知道怎么描述了)的那些选项了吗,对,就是“Your Ensembl”下面那一堆,在里面找“Genomic sequence”,点它
(4)现在的界面就一目了然了,在“5' Flanking sequence”中输入数值确定启动子长度(默认为600),比如1000,点击update;
(5)出现的序列中,标为红色的就是基因的外显子,红色之间黑色的序列就是内含子,而第一个红色自然就是第一外显子了,那么从开始的碱基一直到第一个红色的碱基间自然就是启动子-1000~+1的序列啦
这样,你不仅查到了启动子,连它的外显子、内含子序列也全部搞定了
我以前回的贴,总结一下
共享】如何查找一个基因的启动子序列[BCL-2为例]
定义:启动子是参与特定基因转录及其调控的DNA序列。
包含核心启动子区域和调控区域。
核心启动子区域产生基础水平的转录,调控区域能够对不同的环境条件作出应答,对基因的表达水平做出相应的调节。
区域:启动子的范围非常大,可以包含转录起始位点上游2000bp,有些特定基因的转录区内部也存在着转录因子的结合位点,因此也属于启动子范围。
screen.width-333)this.width=screen.width-333" width=461 height=144 title="Click to view full EukPromoter.gif (461 X 144)" border=0 align=absmiddle>
下面以BCL-2基因为例,查找查找该基因的启动子区域,首先要找到该基因的基因组序列。
去NCBI吧,在Search的下拉菜单里找到Gene,在检索项里输入Bcl-2,检索第一项就是bcl-2 for human,点进去看看啥样。
(缩略图,点击图片链接看原图)
首先你可以看到该基因的参考序列(reference sequence),然后看到bcl-2的位置和基因组背景。
bcl-2上游是PHLPP,下游是FVT1基因。
在这个长长的网页的最后是已经注册的Bcl-2基因的信息。
(缩略图,点击图片链接看原图)
看到基因组序列了么,点进去,根据序列信息自己就能定位转录起始位点,上游就是promoter 了,简单吧。
不!我觉得麻烦。
有更简单的方法么?有!注意到在网页的开头有这么个链接么?HGNC:990
(缩略图,点击图片链接看原图)
点进去,看看吧。
原来是BCL-2的symbol report,各种各样的连接。
注意到左下角的Ensembl GeneView 了么,很有用的,点击。
(缩略图,点击图片链接看原图)
呵呵,原来到了Ensemble了,是Ensemble的report。
列出了一堆令人兴奋的信息,太全了,只要是和这个基因相关的信息都能找到,包括SNP,Isoforms,等等等。
我们感兴趣的是,这个连接“View genomic sequence for this gene with exons highlighted”
(缩略图,点击图片链接看原图)
点击,看看,原来是bcl-2的基因组结构,红底色碱基是exon,绿底色碱基是SNP,太牛了。
别光高兴,忘了找promoter,默认的这个report只是显示bcl-2,上游600bp,下游600bp。
想想,短了一点。
怎么样让5'端多显示几百个碱基呢?秘密在这里。
(缩略图,点击图片链接看原图)
把“5' Flanking sequence”的值改成5000bp,哼!小样!!不行?10000,20000,。
,靠,上一个基因的exon都露出来,算了吧(最大值99999)。
如果保守估计可以做起始位点上游2000bp内的区域,如果最大化估计,可以用起始位点上游至上有基因的最后一个exon结尾处,算你狠!!!
screen.width-333)this.width=screen.width-333" width=457 height=220 title="Click to view full bcl-2-7.jpg (457 X 220)" border=0 align=absmiddle>
然后就分析吧,先到MA TCH分析一下转录因子结合位点。