第四章 DNAman使用方法
- 格式:ppt
- 大小:294.50 KB
- 文档页数:27


生物信息学上机实验四用DNAMAN软件设计PCR引物一、目的要求DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA序列分析工具。
通过本实验,使学生掌握PCR引物的设计方法。
二、实验准备DNAMAN的使用说明书(word文档)一份、DNAMAN软件5.2.2版本、实验分析所用的4个序列见下面。
三、实验内容1、将待分析4个序列装入4个Channel,熟悉Channel的使用方法2、显示“序列(2)”的反向互补序列、互补序列、反向序列3、分析“序列(3)”的限制性酶切位点4、设计一对引物扩增“序列(1)”中的微卫星重复区域四、作业将上述前5项操作所得结果保存到电脑桌面,发到xiaopingjia@(1)CCAGA TGAGCGTGCGTTCGTTCCACGTACGTGTGCTGTGTGAGACGACACA TCT GCACCTGCACGTCAGCACGTACGTGCACCCGGTA TGTGTGCGCGTGTACTTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTCTGAGA TGAGGCCGGA TTCAGGA GCTGCGAGCTCA TAGGCCACAGTCACAGAA TTGCAACGGTACTTCAGTTCAGTCA TCTCCTAGTCCTTGAGAG(2)GGAAAAAAGA TACGTA TGTACA TA TACGTGTACGTGTGTGTGTGTGTGTGTGTGT GTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGAAGCAAAGACA TTGA TA TTGTTGCTGGTGGCGAGGTTGA TGCGCACAGCTCACTCCCGCGCTGACTGACACG(3)GGTCAGCAGAAAGCA TGCCGTAGTCAAACGA TCGACCTAGCTAGTAGCAGTGTG TGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTTTTGCAAAAACCTAGACCTTAGCAGCCTAG(4)CCTGA TTTGGA TCCAACAAAA TGCA TTTGACCA TA TAGTGTGTGTGTGTGTGTGTG TGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTTCACAGTCACAGAA TTGCAACGGTACTTCAGTTCAGTCA TCTCCTAGTCCTTGAGAG(2)题 SEQ DNAMAN2: 172 bp;Composition 57 A; 62 C; 22 G; 31 T; 0 OTHERPercentage: 33.1% A; 36.0% C; 12.8% G; 18.0% T; 0.0%OTHERMolecular Weight (kDa): ssDNA: 52.42 dsDNA: 106.04COLOURSsequence = 1features = 0ORIGIN1 CGTGTCAGTC AGCGCGGGAG TGAGCTGTGC GCATCAACCT CGCCACCAGC AACAATATCA 61 ATGTCTTTGC TTCACACACA CACACACACA CACACACACA CACACACACA CACACACACA 121 CACACACACA CACACACACG TACACGTATA TGTACATACG TATCTTTTTT CCSEQ DNAMAN2: 172 bp;Composition 57 A; 62 C; 22 G; 31 T; 0 OTHERPercentage: 33.1% A; 36.0% C; 12.8% G; 18.0% T; 0.0%OTHERMolecular Weight (kDa): ssDNA: 52.42 dsDNA: 106.04COLOURSsequence = 1features = 0ORIGIN1 CCTTTTTTCT ATGCATACAT GTATATGCAC ATGCACACAC ACACACACAC ACACACACAC 61 ACACACACAC ACACACACAC ACACACACAC ACACACACAC TTCGTTTCTG TAACTATAAC 121 AACGACCACC GCTCCAACTA CGCGTGTCGA GTGAGGGCGC GACTGACTGT GCSEQ DNAMAN2: 172 bp;Composition 31 A; 22 C; 62 G; 57 T; 0 OTHERPercentage: 18.0% A; 12.8% C; 36.0% G; 33.1% T; 0.0%OTHERMolecular Weight (kDa): ssDNA: 53.79 dsDNA: 106.04COLOURSsequence = 1features = 0ORIGIN1 GCACAGTCAG TCGCGCCCTC ACTCGACACG CGTAGTTGGA GCGGTGGTCG TTGTTATAG T 61 TACAGAAACG AAGTGTGTGT GTGTGTGTGT GTGTGTGTGT GTGTGTGTGT GTGTGTGTGT 121 GTGTGTGTGT GTGTGTGTGC ATGTGCATAT ACATGTATGC ATAGAAAAAA GG(3)题 Restriction analysis on DNAMAN3Methylation: dam-No dcm-NoScreened with 180 enzymes, 19 sites foundAluI AG/CT 1: 40BbvI GCAGCNNNNNNNN/ 1: 151BsaOI CGRY/CG 1: 32Bst71I GCAGCNNNNNNNN/ 1: 151DdeI C/TNAG 1: 135DpnI GA/TC 1: 31Fnu4HI GC/NGC 1: 140MaeI C/TAG 4: 37, 41, 129, 144MboI /GATC 1: 29NlaIII CATG/ 1: 17NspI RCATG/Y 1: 17PvuI CGAT/CG 1: 32Sau3AI /GATC 1: 29SphI GCATG/C 1: 17TaqI T/CGA 1: 32XorII CGAT/CG 1: 32List by Site Order17 NlaIII 31 DpnI 37 MaeI 140 Fnu4HI17 SphI 32 TaqI 40 AluI 144 MaeI17 NspI 32 PvuI 41 MaeI 151 BbvI29 Sau3AI 32 BsaOI 129 MaeI 151 Bst71I 29 MboI 32 XorII 135 DdeINon Cut EnzymesAatII Acc65I AccI AccII AccIII AclIAcyI AflII AflIII AgeI AhaIII Alw26IAlw44I AlwNI ApaBI ApaI ApaLI AscIAsp718I AsuI AsuII AvaI AvaII AvrIIBalI BamHI BanI BanII BbeI BbvIIBclI BglI BglII Bpu1102I BsaHI Bsc91IBsiI BsmI Bsp1286I Bsp1407I BspHI BspMIBspMII BssHII BstD102I BstEII BstNI BstXIBsu36I Cfr10I CfrI ClaI Csp45I CspICvnI DraI DraII DraIII DrdI EagIEam1105I Ecl136II Eco31I Eco47III Eco52I Eco56IEco57I Eco72I EcoHI EcoICRI EcoNI EcoRIEcoRII EcoRV EheI EspI FnuDII FokIFseI HaeII HaeIII HgaI HgiAI HhaIHindII HindIII HinfI HinP1I HpaI HpaIIHphI I-PpoI KpnI MaeII MaeIII MboIIMfeI Mlu113I MluI MnlI MscI MseIMspA1I MspI MstI MstII NaeI NarINcoI NdeI NheI NlaIV NotI NruINsiI NspBII PacI PflMI PinAI PleIPmaCI PmeI PpuMI PssI PstI PvuIIRleAI RsaI SacI SacII SalI SapISauI ScaI SciI ScrFI SduI SfaNISfiI SgrAI SmaI SnaBI SpeI SplISpoI SrfI SspI SstI SstII StuIStyI SunI SwaI ThaI Tth111I Tth111IIVspI XbaI XcmI XhoI XhoII XmaIXmaIII XmnIRestriction sites on DNAMAN3MaeIAluIMaeIXorIIBsaOIPvuITaqINspI DpnISphI MboINlaIII Sau3AI1 GGTCAGCAGAAAGCATGCCGTAGTCAAACGATCGACCTAGCTAGTAGCAGTGTGTGTGTGCCAGTCGTCTTTCGTACGGCATCAGTTTGCTAGCTGGATCGATCATCGTCACACACACAC61 TGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTGTTTTACACACACACACACACACACACACACACACACACACACACACACACACACACACACAAAAMaeIMaeI DdeI Fnu4HI121 GCAAAAACCTAGACCTTAGCAGCCTAGCGTTTTTGGATCTGGAATCGTCGGATC(4)题Primer List29 CGTGTGCTGTGTGAGAC 51.9癈 and 224 GGAGATGACTGAACTGAAG 50.1癈30 GTGTGCTGTGTGAGACG 51.9癈 and 224 GGAGATGACTGAACTGAAG 50.1癈32 GTGCTGTGTGAGACGAC 50.7癈 and 224 GGAGATGACTGAACTGAAG 50.1癈。

dnaman使用方法使用DNAMAN的方法DNAMAN是一款功能强大的生物信息学软件,广泛应用于DNA 和蛋白质序列分析、比对、编辑和可视化等领域。
本文将介绍DNAMAN的使用方法,帮助读者快速上手并熟练运用该软件。
一、安装和启动DNAMAN1. 下载软件安装包:在DNAMAN官方网站上下载适用于您的操作系统的安装包,并保存到本地。
2. 安装软件:双击安装包,按照提示完成软件的安装过程。
3. 启动软件:安装完成后,双击桌面上的DNAMAN图标,即可启动软件。
二、导入和编辑序列1. 导入序列:在DNAMAN的主界面,点击"文件"菜单,选择"导入序列",然后选择您要导入的序列文件(支持FASTA、GenBank 等格式)。
2. 编辑序列:在序列编辑界面,您可以对序列进行添加、删除、替换等操作。
点击"编辑"菜单,选择相应的编辑功能,然后在弹出的对话框中进行操作。
三、序列比对和分析1. 序列比对:点击"工具"菜单,选择"序列比对",然后选择比对算法和参数设置,点击"开始比对"按钮即可进行序列比对。
2. 序列分析:DNAMAN提供了丰富的序列分析工具,如ORF预测、限制酶切位点分析、引物设计等。
点击"工具"菜单,选择相应的分析工具,按照提示进行操作。
四、序列可视化和输出1. 序列可视化:DNAMAN提供了多种序列可视化方式,如线性图、环形图、比对图等。
点击"视图"菜单,选择相应的可视化方式,即可查看序列的结构和特征。
2. 输出结果:完成序列分析后,您可以将结果导出为文本文件或图像文件。
点击"文件"菜单,选择"导出结果",然后选择输出格式和保存路径,点击"保存"按钮即可导出结果。
五、保存和管理项目1. 保存项目:在使用DNAMAN进行序列分析时,建议您保存项目以便后续操作。



序列分析软件DNAMAN的使用方法中文演示文稿第一部分:软件介绍1.DNAMAN是什么?-DNAMAN是一款用于DNA和蛋白质序列分析的软件。
-它提供多种功能,包括序列比对、引物设计、限制酶分析和进化树构建等。
2.DNAMAN的应用领域-DNAMAN广泛应用于生物学、生物技术和医药领域。
-它可以帮助研究人员进行序列分析、设计实验方案和解读实验结果。
第二部分:基本序列比对1.创建新项目-打开DNAMAN软件,点击“新建”按钮创建新项目。
-输入项目名称和序列信息,保存并打开该项目。
2.导入序列-点击“导入”按钮,选择需要比对的序列文件,点击“确定”导入。
-系统会自动将序列导入到项目中。
3.序列比对-选择需要比对的序列,点击“比对”按钮进行序列比对。
-系统会自动比对序列并生成比对结果。
4.结果解读-比对结果以图形和文本形式展示。
-可以通过选择不同的比对算法和调整参数来优化比对结果。
第三部分:引物设计1.创建新项目-打开DNAMAN软件,点击“新建”按钮创建新项目。
-输入项目名称和序列信息,保存并打开该项目。
2.导入标记序列-点击“导入”按钮,选择需要设计引物的标记序列文件,点击“确定”导入。
-系统会自动将标记序列导入到项目中。
3.引物设计-点击“引物设计”按钮,选择设计引物的参数和算法。
-系统会根据所选参数和算法自动生成引物设计结果。
4.结果解读-引物设计结果以图形和文本形式展示。
-可以通过选择不同的参数和算法来优化引物设计结果。
第四部分:限制酶分析1.创建新项目-打开DNAMAN软件,点击“新建”按钮创建新项目。
-输入项目名称和序列信息,保存并打开该项目。
2.导入限制酶序列-点击“导入”按钮,选择需要分析的限制酶序列文件,点击“确定”导入。
-系统会自动将限制酶序列导入到项目中。
3.限制酶分析-点击“限制酶分析”按钮,选择分析参数和算法。
-系统会根据所选参数和算法自动进行限制酶分析。
4.结果解读-限制酶分析结果以图形和文本形式展示。


序列比对的理论基础是进化学说:如果两个序列之间具有足够的相似性,就推测二者可能有共同的进化祖先,经过序列内残基的替换、残基或序列片段的缺失、以及序列重组等遗传变异过程分别演化而来。
序列相似和序列同源是不同的概念,序列之间的相似程度是可以量化的参数,而序列是否同源需要有进化事实的验证。
物以类聚人以群分,就像你要了解一个人可以通过了解他的朋友一样,序列比对是从已知获得未知的一个十分有用的方法。
另外,物种亲缘树的构建都需要进行生物分子序列的相似性比较。
序列比对按照数目、范围和对象来分,可以分为:o两序列比对和多序列比对o全局比对和局部比对o核酸序列比对和氨基酸序列比对。
限于篇幅,今天只给大家介绍如何使用DNAMAN 8作核酸多序列比对。
多序列比对就是把两条以上可能有系统进化关系的序列进行比对的方法。
其意义在于它能够把不同种属的相关序列的比对结果按照特定的格式输出,并且在一定程度上反映它们之间的相似性。
首先,在解螺旋回复0628下载DNAMAN 8软件。
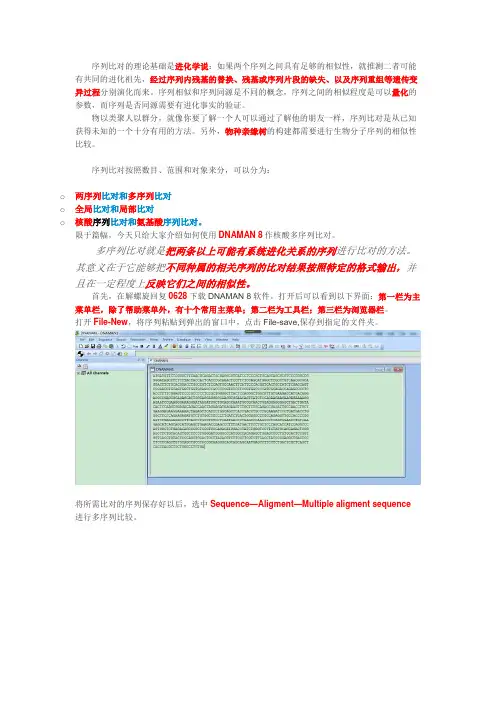
打开后可以看到以下界面:第一栏为主菜单栏,除了帮助菜单外,有十个常用主菜单;第二栏为工具栏;第三栏为浏览器栏。
打开File-New,将序列粘贴到弹出的窗口中,点击File-save,保存到指定的文件夹。
将所需比对的序列保存好以后,选中Sequence—Aligment—Multiple aligment sequence 进行多序列比较。
在弹出的窗口Sequence&Files中加载序列,File、Fold、channel、Database分别表示从文件、文件夹、channel和数据库中获取序列。
勾选窗口中的“DNA”,点击“下一步”。
在弹出的窗口Method中,“optimalaligment”最佳比对方式中有四个高大上的选项:Full Alignment(完全比对)、Prosile Aligment(轮廓比对)、New Swquence on Profile (轮廓上的新序列)、Fast Alignment(快速比对),本文选择了Fast Alignment,并且勾选了Try both strands(尝试使用双链)。

DNAMAN的使用方法DNAMAN是一种快速、准确、高通量的DNA检测工具,可以用于各种生物学研究和临床应用中。
DNAMAN的使用非常简单,但有一些关键步骤和注意事项需要注意。
以下是DNAMAN的详细使用方法,以帮助您充分利用这个工具。
第一步:准备样本第二步:DNA提取DNA提取是DNAMAN使用的关键步骤,它有助于从样本中纯化和分离出DNA。
您可以使用商用的DNA提取试剂盒,按照说明书中的步骤进行操作。
确保遵循所有操作步骤,并注意避免任何与其他样本的交叉污染。
第三步:DNA定量第四步:稀释DNA根据DNAMAN的说明书,使用PBS或其他适当的缓冲溶液将DNA稀释到所需的浓度。
确保在实验室条件下进行稀释,并遵循操作规范,以避免任何误差。
第五步:添加DNA至DNAMAN芯片将稀释后的DNA样品添加到DNAMAN芯片中的指定位置。
根据芯片的标记,确保每个样品正确放置,并避免任何交叉污染。
如果需要,可以使用多通道移液器进行操作,以提高效率。
第六步:启动DNAMAN分析在DNAMAN分析仪上启动相应的分析程序。
根据仪器的说明书,选择适当的参数和设置。
确保校准仪器,以获得准确的结果。
第七步:数据收集和解读注意事项:1.在操作DNAMAN之前,确保您已经熟悉仪器的说明书和操作流程。
遵循所有操作规程,以确保准确性和结果的可靠性。
2.在使用DNAMAN之前,请确保仪器已经进行了校准和维护,并且仪器状态良好。
如有必要,请进行常规性能检查,并在需要时进行任何维护和修理。
3.在操作中避免交叉污染。
使用带有盖子的离心管和一次性移液器尖,避免任何样品之间的接触。
4.尽量减少操作时间,以避免DNA的降解。
在整个实验过程中,尽量保持操作环境的清洁和无尘。
5.定期评估和验证DNAMAN的性能。
与其他方法进行对比试验,以确保DNAMAN的结果的准确性和可靠性。
总结:DNAMAN是一种非常有用的DNA检测工具,可以在各种生物学研究和临床应用中得到应用。
序列分析软件DNAMAN的使用方法简介吕惠平(新疆大学生命科学与技术学院;新疆生物资源基因工程重点实验室,乌鲁木齐,830046) DNAMAN是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA序列分析工具。
本文以DNAMAN 5.2.9 Demo version为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为浏览器栏:在浏览器栏下方的工作区左侧,可见Channel工具条,DNAMAN提供20个Channel,(如左所示:)点击Channel工具条上相应的数字,即可击活相应的Channel。
每个Channel可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel中可以节约存取序列时间,加快分析速度。
此版本DNAMAN提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的 Channel中。
本文以具体使用DNAMAN的过程为例来说明如何使用DNAMAN分析序列。
1.将待分析序列装入Channel(1)通过File Open命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
(2)通过Sequence/Load Sequence菜单的子菜单打开文件或将选定的部分序列装入Channel。
通过Sequence/Current Sequence/Analysis Defination命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence//Display Sequence命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
DNAMAN使用说明书DNAMAN 是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA 序列分析工具。
本文以DNAMAN 5.2.9 Demo version 为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为浏览器栏:在浏览器栏下方的工作区左侧,可见Channel 工具条,DNAMAN 提供20 个Channel,(如左所示:)点击Channel 工具条上相应的数字,即可击活相应的Channel。
每个Channel 可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel 中可以节约存取序列时间,加快分析速度。
此版本DNAMAN 提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的Channel 中。
本文以具体使用DNAMAN 的过程为例来说明如何使用DNAMAN 分析序列。
1.将待分析序列装入Channel(1)通过File Open 命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
(2)通过Sequence/Load Sequence 菜单的子菜单打开文件或将选定的部分序列装入Channel 。
通过Sequence/Current Sequence/Analysis Defination 命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence//Display Sequence 命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。
对话框选项说明如下:Sequence &Composition 显示序列和成分Reverse Complement Sequence 显示待分析序列的反向互补序列Reverse Sequence 显示待分析序列的反向序列Complement Sequence 显示待分析序列的互补序列Double Stranded Sequence 显示待分析序列的双链序列RNA Sequence 显示待分析序列的对应RNA 序列3.DNA 序列的限制性酶切位点分析将待分析的序列装入Channel,点击要分析的Channel,然后通过Restriction/Analysis 命令打开对话框,如下所示:参数说明如下:Results 分析结果显示其中包括:Show summary(显示概要) Show sites on sequence(在结果中显示酶切位点)Draw restriction map(显示限制性酶切图)Draw restriction pattern (显示限制性酶切模式图)Ignore enzymes with more than(忽略大于某设定值的酶切位点)Ignore enzymes with less than(忽略小于某设定值的酶切位点)Target DNA (目标DNA 特性)circular(环型DNA),dam/dcm methylation(dam/dcm 甲基化)all DNA in Sequence Channel(选择此项,在Sequence Channel 中的所有序列将被分析,如果选择了Draw restriction pattern,那么当所有的channel 中共有两条DNA 时,则只能选择两个酶分析,如果共有三个以上DNA 时,则只能用一个酶分析。
水天2014.11.3编辑
DNAMAN 是美国 Lynnon Biosoft 公司开发的高度集成化的分子生物学综合应用软件,可以用于多序列比对、PCR 引物设计、限制性酶切分析、质粒绘图、蛋白质分析等,几乎囊括了所有日常核酸、蛋白质序列的分析工作。
下面是软件界面截图的操作流程以及简单说明,其他的一些功能可以自己摸索,都比较简单。
这个软件很容易找到汉化版,一般都没有功能限制,而且很好的一点就是可以保存所有的比对和分析结果!!有木有,这一点太赞了。
First.DNA
多序列比对
可以批量载入测序结果以及参考序列
在比对方式的选择上,一般选完全比对和快速比对,其他参数一般默认。
其中完全比对只能同时比对一个方向的测序结果,如果正反向同时进入比对,反向会和正向从一边开始比对,当然就比对不上了。
而快速比对可以正反向批量比对。
生物分析软件DNAMAN 简单使用方法
2014年11月3日9:59
2.限制性酶切分析
限制性酶切分析需要首先载入目标序列
选择合适的酶文件以及想要看到的信息,下一步就OK了
我的示例序列的分析结果。
序列分析软件DNAMAN的使用方法简介吕惠平(新疆大学生命科学与技术学院;新疆生物资源基因工程重点实验室,乌鲁木齐,830046) DNAMAN是一种常用的核酸序列分析软件。
由于它功能强大,使用方便,已成为一种普遍使用的DNA序列分析工具。
本文以DNAMAN 5.2.9 Demo version为例,简单介绍其使用方法。
打开DNAMAN,可以看到如下界面:第一栏为主菜单栏。
除了帮助菜单外,有十个常用主菜单,第二栏为工具栏:第三栏为浏览器栏:在浏览器栏下方的工作区左侧,可见Channel工具条,DNAMAN提供20个Channel,(如左所示:)点击Channel工具条上相应的数字,即可击活相应的Channel。
每个Channel可以装入一个序列。
将要分析的序列(DNA 序列或氨基酸序列)放入Channel中可以节约存取序列时间,加快分析速度。
此版本DNAMAN提供自动载入功能,用户只需激活某个Channel,然后打开一个序列文件,则打开的序列自动载入被激活的 Channel中。
本文以具体使用DNAMAN的过程为例来说明如何使用DNAMAN分析序列。
1.将待分析序列装入Channel(1)通过File Open命令打开待分析序列文件,则打开的序列自动装入默认Channel。
(初始为channel1)可以通过激活不同的channel (例如:channel5)来改变序列装入的Channel。
(2)通过Sequence/Load Sequence菜单的子菜单打开文件或将选定的部分序列装入Channel。
通过Sequence/Current Sequence/Analysis Defination命令打开一个对话框,通过此对话框可以设定序列的性质(DNA 或蛋白质),名称,要分析的片段等参数。
2.以不同形式显示序列通过Sequence//Display Sequence命令打开对话框,如下图所示:根据不同的需要,可以选择显示不同的序列转换形式。