生物信息学 第5章 常用分析软件概论
- 格式:ppt
- 大小:618.50 KB
- 文档页数:13



生物信息学软件
生物信息学软件是一类专门用于处理、分析和解释生物学
数据的软件工具。
这些软件通常用于基因组学、蛋白质组学、转录组学和代谢组学研究中。
以下是一些常用的生物
信息学软件:
1. BLAST:用于快速在数据库中搜索相似序列的工具,对
于序列比对和亲缘关系分析非常有用。
2. ClustalW:用于多序列比对的软件,可以比较多个序列
之间的相似性和差异。
3. GROMACS:用于分子动力学模拟和分子力学计算的软件,可以模拟蛋白质、核酸等生物分子的结构和动态行为。
4. PHYLIP:用于构建进化树和系统发育分析的软件,可以根据序列的差异性推断出生物物种之间的进化关系。
5. R:一种统计软件,提供了广泛的生物信息学功能和数据处理方法。
6. Cytoscape:用于网络分析和可视化的软件,可以分析和可视化基因调控网络、蛋白质相互作用网络等。
7. NCBI工具包:由美国国家生物技术信息中心(NCBI)开发的一组工具,包括BLAST、Entrez等,用于生物序列和文献检索。
8. Galaxy:一个基于云计算的生物信息学分析平台,提供了大量的工具和工作流,方便生物学家进行数据分析和可视化。
9. MetaboAnalyst:用于代谢组学数据分析的软件,可以进行代谢物注释、统计分析、通路分析等。
10. Geneious:用于序列分析和比对、系统发育分析、基因预测等多种生物信息学任务的集成软件。
以上只是一小部分常用的生物信息学软件,随着科学研究的进展,新的软件工具不断涌现。



生物信息学分析工具的使用教程导言:在生物学领域中,随着高通量测序技术的快速发展,生物信息学分析工具的应用变得越来越重要。
这些工具能够帮助研究人员进行基因组、转录组、蛋白质组等大规模数据的分析和解释。
本文将为您介绍几种常用的生物信息学工具,并提供详细的使用指南。
一、BLAST(基因序列比对工具)BLAST(Basic Local Alignment Search Tool)是最常用的生物信息学工具之一,用于比对基因或蛋白质序列中的相似性。
以下是使用BLAST的步骤:1. 打开NCBI网站的BLAST页面,并选择适当的BLAST程序(如BLASTn、BLASTp等)。
2. 将查询序列粘贴到"Enter Query Sequence"框中,或者上传一个FASTA格式的文件。
3. 选择适当的数据库,如"nr"(非冗余序列数据库)或"refseq_rna"(已注释的RNA序列数据库)。
4. 设置相似性阈值、期望值和其他参数。
5. 点击"BLAST"按钮开始比对。
6. 结果页面会显示比对结果的列表和详细信息,包括匹配上的序列、相似性得分等。
二、DESeq2(差异表达基因分析工具)DESeq2是一种用于差异表达基因分析的R包。
以下是使用DESeq2的步骤:1. 安装R语言和DESeq2包。
2. 将基因表达矩阵导入R环境中,并进行预处理(如去除低表达基因)。
3. 根据实验设计设置条件和组别。
4. 进行差异分析,计算基因的表达差异和显著性。
5. 可视化差异表达基因的结果,如绘制散点图、MA图、热图等。
三、GSEA(基因集富集分析工具)GSEA(Gene Set Enrichment Analysis)是一种基于基因集的富集分析方法,用于识别与特定性状或实验条件相关的生物学功能。
以下是使用GSEA的步骤:1. 准备基因表达矩阵和相关的分组信息。


生物信息学分析
生物信息学分析是一种通过对生物序列、蛋白质结构和文献数据的分析,来探索生物相关问题的方法。
该分析包括基因组分析、转录组分析、蛋白质结构分析以及各种其他生物学分析。
基因组分析是生物信息学中最重要的部分,它用于探索基因的位置、功能和表达水平。
常用的工具包括BLAST、ClustalW、GeneFinder以及其他软件。
转录组分析用于探索基因的表达模式。
这个分析可以用来确定哪些基因在不同细胞类型中被表达,以及在不同条件下它们的表达水平如何变化。
蛋白质结构分析用于探索蛋白质的结构和功能。
它可以用来研究蛋白质之间的相互作用,也可以用来确定蛋白质的结构和功能。
常用的工具包括T-Coffee、Molecule Viewer以及其他软件。
此外,生物信息学分析还可以用于探索遗传变异、致病机制、治疗策略以及其他生物学研究问题。

生命科学中常用的软件及其应用生命科学是一个涉及多个学科交叉的领域,其中运用到的软件非常丰富。
这些软件可以帮助生命科学研究人员完成从基因组测序到蛋白质结构分析的各种复杂任务。
在这篇文章中,我们将介绍一些生命科学中常用的软件及其应用,帮助读者更好地了解这个领域。
1. BLASTBLAST(基本局部序列比对工具)是基因组测序领域中最常用的软件之一。
它可以在数据库中进行序列比对,并根据相似性评分进行排序和过滤。
BLAST的应用非常广泛,包括在基因组测序和蛋白质结构分析中用于序列比对,DNA和蛋白质序列注释,以及进化分析等。
2. CLC Genomics WorkbenchCLC Genomics Workbench是一个功能强大的基因组分析软件,可以用于基因组测序和生物信息学分析。
它可以处理各种不同类型的数据,包括RNA测序数据、DNA测序数据和蛋白质序列数据。
使用该软件,科学家可以进行基因组组装、基因表达分析、SNP检测、CNV分析等多种复杂的分析任务。
3. PyMOLPyMOL是一个用于分子可视化和分析的软件。
它可以用于可视化蛋白质、DNA和RNA结构,以及与其他分子的相互作用。
在生物学研究中,PyMOL被广泛用于研究蛋白质结构和功能。
化学公式、分子等多种形式,都能够被轻松制作出来。
4. RR是一个免费的数据分析软件,主要用于统计分析、数据可视化和预测模型的建立。
在生命科学中,R被广泛用于基因表达分析、蛋白质结构预测、生存分析等多个领域。
它是生命科学研究者进行大规模数据分析的首选工具之一。
5. CytoscapeCytoscape是一款网络分析软件,用于研究生物分子间的相互作用,例如蛋白质-蛋白质相互作用,基因调控网络等。
Cytoscape具有丰富的图形界面,可以使用各种插件来进行网络建模、可视化和分析。
6. HMMERHMMER是用于进行隐马尔可夫模型(HMM)建模和分析的工具软件。
在生命科学领域,HMMER被用于进行蛋白质序列比对和蛋白质家族分类。
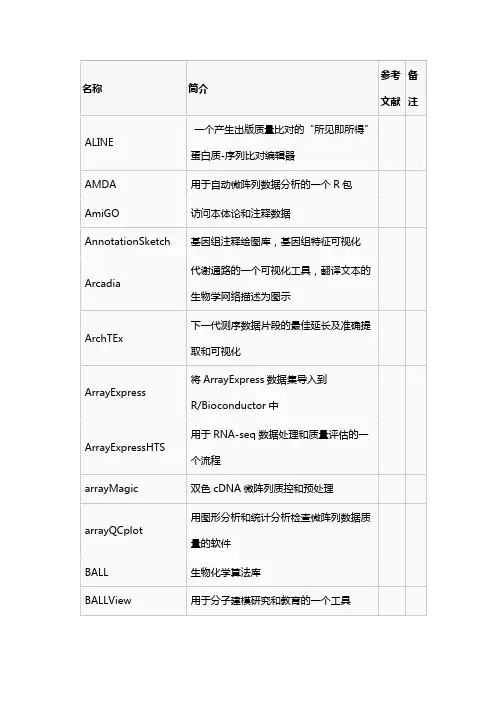

生物信息学分析工具的使用与解释方法生物信息学是一门研究生物学领域中的大量数据,通过计算机科学技术和统计学方法进行分析和解释的学科。
在现代生物学研究中,生物信息学工具的使用已经成为了一项必不可少的技术手段。
本文将介绍几种常用的生物信息学分析工具及其使用方法,并对其解释方法进行详细说明。
1. BLAST (Basic Local Alignment Search Tool)BLAST是生物信息学领域中最常用的工具之一,用于比对和分析生物序列。
其主要功能是在数据库中寻找与查询序列相似的序列,并将相似度高的序列进行排序和归类。
BLAST可以帮助研究人员确定一个不熟悉的生物序列的功能、相似序列的来源以及进行物种演化分析等。
使用BLAST时,用户需将待比对的序列输入到工具中,选择合适的比对参数,并选择合适的参考数据库进行搜索。
BLAST会返回一系列比对结果,其中包含了序列相似度、数据库匹配的统计信息等。
2. RNA-Seq (RNA sequencing)RNA-Seq 是一种高通量测序技术,用于测定转录组的RNA序列信息。
它可以帮助研究人员了解基因表达的水平及其调控机制。
使用RNA-Seq时,首先需要将RNA提取和逆转录为互补DNA(cDNA),然后通过高通量测序将cDNA片段测定出来。
接下来,对测序数据进行预处理,包括过滤低质量序列和去除测序接头等。
最后,使用合适的生物信息学工具对测序数据进行定量分析、差异表达分析等。
例如,可以使用Tophat、HISAT等软件对RNA-Seq数据进行比对和定量分析,使用DESeq2、edgeR等软件对基因表达差异进行统计和可视化分析。
3. GO (Gene Ontology)Gene Ontology 是一套用于描述基因功能的标准化的基因注释信息系统。
它提供了一个标准化的词汇库和定义,用于描述基因、蛋白质及其相关性状和功能。
GO具有三个主要分类,包括分子功能(Molecular Function)、细胞组分(Cellular Component)和生物过程(Biological Process)。
生物信息学中的数据分析方法及工具推荐生物信息学是一门充满挑战和机遇的交叉学科,借助于计算机科学和统计学的技术,研究生物学中的大规模数据。
随着高通量测序技术的发展,生物学家们可以获取大量的生物学数据,如基因表达数据、DNA序列数据和蛋白质结构数据等。
而为了更好地理解和利用这些数据,生物信息学中的数据分析方法和工具起到了至关重要的作用。
本文将介绍一些在生物信息学中常用的数据分析方法和工具,并分析其特点。
1. 序列比对工具序列比对是生物信息学的基本任务之一,用于将已知的DNA或蛋白质序列与未知序列进行比较,从而确定它们之间的相似性和差异性。
在序列比对中,常用的工具包括BLAST(Basic Local Alignment Search Tool)和Bowtie。
BLAST通过在数据库中搜索相似序列,从而识别未知序列的亲缘关系。
而Bowtie是一种用于高通量测序数据比对的工具,具有快速、准确和高效的特点。
2. 基因表达分析工具基因表达数据的分析是生物信息学中的关键任务之一,可以用于了解基因在生物体中的功能和调控机制。
在基因表达分析中,常用的工具包括DESeq2和edgeR。
这些工具能够分析RNA测序数据,识别差异表达基因,并进行功能注释和通路分析。
3. 蛋白质结构预测工具蛋白质结构预测是生物信息学中的一项重要任务,可以揭示蛋白质的功能和三维结构信息。
在蛋白质结构预测中,常用的工具包括I-TASSER和Rosetta。
I-TASSER利用模板比对和蛋白质碎片装配的方法,预测蛋白质的三维结构。
而Rosetta是一种基于物理能量和碰撞振荡的方法,能够进行蛋白质折叠和构象搜索。
4. 基因组注释工具基因组注释是对基因组序列中的基因和非编码区域进行注释和功能预测的过程。
在基因组注释中,常用的工具包括Ensembl和NCBI的Basic Local Alignment Search Tool (BLAST)。
Ensembl提供了大量的物种基因组注释信息,包括基因结构、启动子、转录因子结合位点等。
生信分析软件都有哪些?生信分析软件在生物信息学研究中可以帮助研究人员处理、分析和解释生物学数据,从而揭示生物学系统的结构和功能。
如数据处理和格式转换、序列比对和测序数据分析、基因组注释和功能预测、基因表达分析、变异检测和遗传分析、数据可视化等软件功能都可以提高研究效率和数据解读的准确性。
目前生信分析软件有很多种,笔者总结了部分生信分析软件的主要功能及作用,帮助大家更好的选用目标分析软件,排名部分先后:①BioXFinder国内第一个也是一个生物信息数据库,集成了BLAST、生存分析、基因ID转换等生信分析工具。
汇集了核酸、蛋白、蛋白结构、代谢通路和信号通路信息,可高效的搜寻到自己想要的信息(中英双文),并且在无代码的情况下完成生信分析。
举例工具Ⅰ:生存分析图生存分析图功能说明研究某癌症类型中患者的生存情况研究biomarker在癌症中的预后效果研究不同分组之间患者的生存是否存在差异数据输入说明支持txt(制表符分隔)文本文件、csv(逗号分隔)文本文件、以及Excel专用的xlsx格式,以及Excel的xls格式。
输入的数据共三列:第1列(生存时间列):如总生存期、无病生存期、无进展生存期等等,数值为生存天数。
第2列(终点事件列):为二分类变量0或1,1对应终点事件结局(如患者死亡,疾病痊愈等)。
第3列(分组信息列):分类型数据,如男/女、抽烟/不抽烟。
若想要探究的数据为连续型变量,如年龄、基因表达量、风险评分等等,需自行划分分组,如根据中位数将目标基因表达量拆分为高表达、低表达两组,将风险评分拆为高风险、低风险两组,将年龄拆分为幼年、青年、中年、老年等。
参数说明根据自身需求选择是否需要在生存分析主图中显示风险表、删失表、置信区间、P值和中位生存时间线;每个表中的参数可根据需求选择相对应的值。
运行结果说明横轴表示时间轴,纵轴表示生存概率。
不同曲线的颜色,对应相应分组的生存曲线。
经过logrank 检验后发现P 值= 0.0001 < 0.05,表明不同分组的患者生存状况的差异不能用抽样误差来解释,分组因素才是导致两条曲线生存率出现差异的原因。
生物信息学分析工具的操作指南与使用技巧近年来,随着生物学研究的向深度学习和大数据方向转变,生物信息学分析工具越来越重要。
这些工具能够处理和解读庞大的生物信息数据,从而提供对基因、蛋白质和其他生物分子功能的深入了解。
为了帮助研究者更好地应用这些工具,本文将提供生物信息学分析工具的操作指南与使用技巧。
一、 BLASTBLAST(Basic Local Alignment Search Tool)是最常用的生物信息学工具之一,用于比对基因或蛋白质序列并寻找相似性。
以下是使用BLAST的操作指南:1. 登录NCBI(National Center for Biotechnology Information)网站,选择"BLAST"选项卡。
2. 选择合适的BLAST程序,如nucleotide BLAST(用于比对核苷酸序列)或protein BLAST(用于比对蛋白质序列)。
3. 输入待比对的序列或上传序列文件。
4. 选择适当的数据库进行比对。
例如,对于人类基因,可以选择"Human genome"数据库。
5. 调整BLAST参数,如期望阈值(E-value)和比对长度,以优化结果。
6. 提交任务并等待结果。
BLAST将返回比对结果和相似性分数。
使用技巧:- 选择正确的数据库,以确保比对结果具有生物学相关性。
- 调整参数以满足特定的研究需求,如提高灵敏度或选择严格的相似性阈值。
- 分析比对结果时,关注较高的BLAST分数和较低的E-value,以确定最相关的序列。
二、DNA序列编辑器DNA序列编辑器是生物信息学研究中常用的工具,用于编辑、操作和分析DNA序列。
以下是使用DNA序列编辑器的操作指南:1. 下载和安装合适的DNA序列编辑器,如ApE(A plasmid Editor)或SnapGene。
2. 打开编辑器并创建新项目。
3. 在序列窗口中输入或粘贴DNA序列。
生物信息学数据分析与应用作业指导书第1章绪论 (3)1.1 生物信息学概述 (3)1.2 数据分析在生物信息学中的应用 (3)1.3 生物信息学数据分析方法与工具 (4)第2章基因组学与遗传数据分析 (4)2.1 基因组测序技术 (4)2.1.1 测序技术原理及发展 (4)2.1.2 测序数据产出及质量控制 (4)2.2 基因组组装与注释 (5)2.2.1 基因组组装 (5)2.2.2 基因组注释 (5)2.3 遗传变异分析 (5)2.3.1 遗传变异检测 (5)2.3.2 遗传变异注释 (5)第3章转录组学与表达数据分析 (5)3.1 转录组测序技术 (5)3.2 表达量定量与标准化 (6)3.3 差异表达基因分析 (6)第4章蛋白质组学与质谱数据分析 (6)4.1 蛋白质组学技术 (6)4.1.1 双向凝胶电泳 (7)4.1.2 蛋白质芯片 (7)4.1.3 液相色谱质谱联用技术 (7)4.1.4 定量蛋白质组学技术 (7)4.2 质谱数据分析 (7)4.2.1 质谱数据分析流程 (7)4.2.2 常用质谱数据分析软件 (7)4.3 蛋白质相互作用网络分析 (7)4.3.1 蛋白质相互作用数据获取 (7)4.3.2 蛋白质相互作用网络的构建 (8)4.3.3 蛋白质相互作用网络分析 (8)第5章系统生物学与网络分析 (8)5.1 系统生物学概述 (8)5.2 生物分子网络构建 (8)5.3 网络拓扑属性分析 (8)第6章生物信息学数据库与数据挖掘 (9)6.1 生物信息学数据库简介 (9)6.2 数据挖掘方法与应用 (9)6.3 基因本体与通路分析 (9)第7章单细胞数据分析 (9)7.1 单细胞测序技术 (10)7.1.2 单细胞测序技术发展 (10)7.1.3 单细胞测序应用 (10)7.2 单细胞表达量数据分析 (10)7.2.1 数据预处理 (10)7.2.2 差异表达分析 (10)7.2.3 细胞周期和批次效应校正 (10)7.3 单细胞轨迹推断与聚类分析 (11)7.3.1 单细胞轨迹推断 (11)7.3.2 单细胞聚类分析 (11)7.3.3 聚类结果的验证与解读 (11)第8章空间转录组数据分析 (11)8.1 空间转录组技术 (11)8.2 空间转录组数据预处理 (11)8.2.1 数据质量控制 (12)8.2.2 数据标准化 (12)8.2.3 数据校正 (12)8.3 空间基因表达模式分析 (12)8.3.1 空间基因表达差异分析 (12)8.3.2 空间基因表达聚类分析 (12)8.3.3 空间基因共表达网络分析 (12)8.3.4 空间基因表达模式可视化 (12)第9章人工智能在生物信息学中的应用 (13)9.1 机器学习与深度学习基础 (13)9.1.1 机器学习简介 (13)9.1.2 深度学习简介 (13)9.2 生物信息学中的应用实例 (13)9.2.1 基因表达分析 (13)9.2.2 蛋白质结构预测 (13)9.2.3 疾病诊断与预测 (13)9.3 基于的药物设计与筛选 (13)9.3.1 药物分子设计 (13)9.3.2 药物靶点预测 (14)9.3.3 药物筛选与优化 (14)第10章生物信息学综合案例分析 (14)10.1 案例一:肿瘤基因组数据分析 (14)10.1.1 数据收集与预处理 (14)10.1.2 基因组变异检测 (14)10.1.3 变异功能注释 (14)10.1.4 基因集富集分析 (14)10.2 案例二:植物抗逆转录组分析 (14)10.2.1 数据收集与预处理 (15)10.2.2 差异表达基因分析 (15)10.2.3 功能注释与分类 (15)10.3 案例三:微生物组数据分析与应用 (15)10.3.1 数据收集与预处理 (15)10.3.2 微生物组成分析 (15)10.3.3 功能预测与注释 (15)10.3.4 微生物组与环境因素关联分析 (15)10.4 案例四:药物靶点发觉与验证分析 (15)10.4.1 药物靶点筛选 (16)10.4.2 靶点功能注释 (16)10.4.3 靶点验证 (16)10.4.4 靶点网络分析 (16)第1章绪论1.1 生物信息学概述生物信息学是一门新兴的交叉学科,融合了生物学、计算机科学、数学、统计学等多个领域的知识。
生物信息学分析工具使用指南生物信息学是一门综合性学科,涵盖了生物学、计算机科学和数学等多个学科领域。
生物信息学的发展为生命科学研究提供了强大的工具和方法,其中生物信息学分析工具是其中最重要的一部分。
本文将介绍常用的生物信息学分析工具,并提供使用指南。
一、序列分析工具1. BLASTBLAST(Basic Local Alignment Search Tool)是一种快速比对局部序列相似性的工具。
它主要用于对基因、蛋白质及其他生物序列进行比对和标定。
使用BLAST,我们可以找到与已知序列相似的未知序列,并推测其功能。
使用提示:将待比对序列输入BLAST程序中,选择合适的数据库进行比对。
根据结果的相似性、E值和比对长度等指标进行评估和选择。
结果的解读需要结合生物学背景知识进行分析。
2. ClustalWClustalW是一种常用的多序列比对软件,可用于比对DNA、RNA和蛋白质序列。
它能够找出多个序列之间的保守区域和差异区域,从而推测序列的结构和功能。
使用提示:将待比对序列输入ClustalW程序中,进行多序列比对。
可以选择不同的参数设置,如输出格式、权重矩阵和树状图构建等。
二、基因表达分析工具1. RNA-SeqRNA-Seq是一种常用的高通量测序技术,用于研究基因的表达。
它通过测量转录本的序列,可以定量、全面地分析基因表达的差异和变化。
使用RNA-Seq,可以发现新的转录本、剪切变异和基因融合等。
使用提示:选择合适的测序平台和实验流程,包括RNA的提取、文库构建和测序。
使用不同的数据分析软件,如Tophat、Cufflinks和DESeq2,可以进行数据质控、比对、转录本定量和差异表达分析。
2. Gene Set Enrichment Analysis (GSEA)GSEA是一种常用的基因集富集分析方法,用于揭示基因组中与特定生物学过程或功能相关的基因集。
使用GSEA,我们可以了解某个基因集在特定条件下的富集情况,从而推断其参与的生物学过程或通路。