怎样使用MEGA建立进化树
- 格式:doc
- 大小:669.50 KB
- 文档页数:6
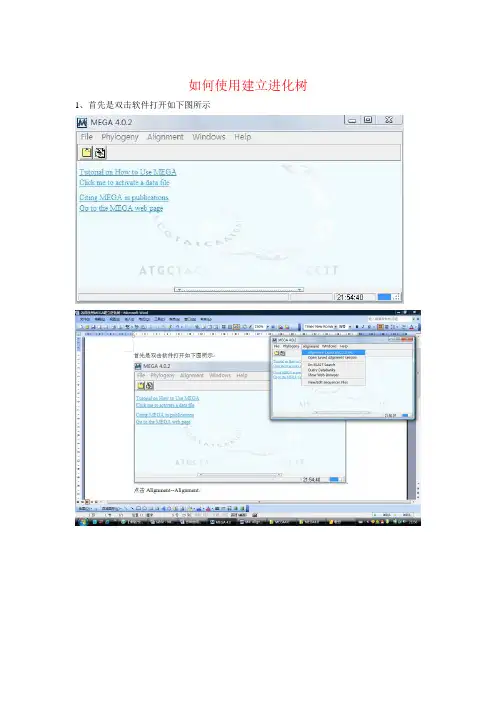
如何使用建立进化树1、首先是双击软件打开如下图所示
2、现在是处于DNA序列,而我们要做蛋白质的进化树的话,就如下操作
3、接下来我们要进行序列的输入,点击左边那个红箭头,则出现下面的窗口;
4、然后右击sequence 1,修改名字,如改成DPV
5、然后从Word 里复制蛋白质序列,然后在下面的位置粘贴
6、则可出现如下图的序列了
7、然后点击窗口上的保存图标保存
8、重复从3开始,直到你的序列输入完
9、序列输入完后进行最后的保存,方法如下:
要输入ul7两次保存名字—然后关闭这个窗口; 接下来打开
出现下面这个窗口
接下来就可以建立各种样式的进化树
嗯,只是把过程写出来,方便大家建立进化树,不足的地方,大家补充好。

1.MEGA构建系统进化树的步骤2.CLUSTALX进行序列比对1.MEGA构建系统进化树的步骤1. 将要用于构建系统进化树的所有序列合并到同一个fasta格式文件,注意:所有序列的方向都要保持一致( 5’-3’)。
如图:2. 打开MEGA软件,选择"Alignment" - "Alignment Explorer/CLUSTAL",在对话框中选择Retrieve sequences from a file, 然后点OK,找到准备好的序列文件并打开,如图:。
3. 在打开的窗口中选择”Alignment”-“Align by ClustalX” 进行对齐,对齐过程需要一段时间,对齐完成后,最好将序列两端切齐,选择两端不齐的部分,单击右键,选择delete即可,如图:。
4. 关闭当前窗口,关闭的时候会提示两次否保存,第一次无所谓,保存不保存都可以,第二次一定要保存,保存的文件格式是.meg。
根据提示输入Title,然后会出现一个对话框询问是否是Protein-coding nucleotide sequence data, 根据情况选择Yes或No。
最后出现一个对话框询问是否打开,选择Yes,如图:。
5. 回到MEGA主窗口,在菜单栏中选择”Phylogeny”-“Bootstrap Test of Phylogeny” -“Neighbor-joining”,打开一个窗口,里面有很多参数可以设置,如何设置这些参数请参考详细的MEGA说明书,不会设置就暂且使用默认值,不要修改,点击下面的Compute按钮,系统进化树就画出来了,如图:在菜单栏中选择”Phylogeny”-“Bootstrap Test of Phylogeny” –“Minimun-evolution”,如图:在菜单栏中选择”Phylogeny”-“Bootstrap Test of Phylogeny” –“Maximun-parsimony”,如图:在菜单栏中选择”Phylogeny”-“Bootstrap Test of Phylogeny” –“UPGMA”,如图:6. 最后,使用TreeExplorer窗口中提供的一些功能可以对生成的系统进化树进行调整和美化。

生物学利用MEGA5.0和Clustalx1.83软件构建进化树MEGA是一个关于序列分析以及比较统计的工具包,从3.1版本到后来的4.0版本一直都广为大家熟悉,现在推出了Mega5.0版本。
功能比以前多有改进。
现主要介绍使用Mega 5.0构建系统进化树的方法。
供大家参考。
用MEGA构建进化树有以下步骤:1、测序:将克隆扩增测序得到的16S rDNA序列进行测序。
2、NCBI上做Blast找到相似度最高的几个序列,确定一下你分离的细菌大约属于哪个科哪个属,如果相似度达到百分之百那基本可以确定你分离得到的就是Blast到的那个,然后寻找相似性最高的细菌,通常把该属的序列(Fasta格式文件)下载下来,或点击GenBank登录号,复制FSATA 格式,整合在一个*.txt文档中(单独建立一个文件夹存放,后面的很多文件会自动装入该文件夹),如>XXXXAGGCTTAACACA TGCAAGTCGAGCGGAGCGAGGGTGCTTGCACCTTAGCTTAGCGGCG GACGGGTGAGTAA TGCTTAGGAA TCTGCCTA TTAGTGGGGGACAACATTCCGAAAGGA ATGCTAATACCGCATACGCCCTACGGGGGAAAGCAGGGGATCTTCGGACCTTGCGCTAA TAGATGAGCCTAAGTCGGA TTAGCTAGTTGGTGGG>gi|289469964|gb|GU388381.1| Acinetobacter tandoii strain DSM 14970 16S ribosomal RNA gene, partial sequence ACTTAGCGGCGGACGGGTGAGTAATGCTTAGGAATCTGCCTATTAGTGGGGGACAACA TTCCGAAAGGGATGCTAATACCGCA TACGCCCTACGGGGGAAAGCAGGGGATCTTCGG ACCTTGCGCTAATAGATGAGCCTAAGTCGGATTAGCTAGTTGGTGGGGTAAAGGCCTAC CAAGGCGACGA TCTGTAGCGGGTCTGAGAGGATGA………………………….参考序列选择注意事项:1、不选非培养(unclutured)微生物为参比;2、不选未定分类地位的微生物,最相近的仅作参考;c,在保证同属的前提下,优先选择16S rDNA全长测序或全基因组测序的种;d,每个种属选择一个参考序列,如果自己的序列中同一属的较多,可适当选择两个参考序列。

干货师兄,我想用MEGA建个树,咋整?作者:解螺旋.冬至转载需授权并注明来源:解螺旋,医生科研助手师妹:师兄,我想建个树。
师兄:啥树啊!你家的family tree啊?师妹:师兄,你不要调戏我,我就建一个简单的进化树!这个怎么做啊?简单呀,你可以用MEGA,先去MEGA官网(/)下载这个软件,免费的啊。
MEGA(Molecular Evolutionary Genetics Analysis )是一个功能非常强大的分子进化遗传分析软件,可用于序列比对、进化树的推断、估计分子进化速度、验证进化假说等。
下面师兄给你详细介绍如何利用Mega软件构建进化树。
1.首先将需要进行建树的序列保存为fasta格式,并将文件扩展名改为.fasta。
.fasta序列格式以“>”开头。
“>”后面这一行写名称,回车,下一行写序列,氨基酸序列类似,所有序列保存在一个txt文件中。
例如:>gene1/speciesname NCBI accession numberATCGGCGTAGCTAGATGCTAGTATCGTA>gene1/speciesname NCBI accession numberAGTAGCTAGTGATGTA2. 点击Align--Edit/built Alignment,选择创建一个新的比对,点OK根据要求选择DNA或者蛋白质序列3.打开需要比对的.fasta文件4. 点击Alignment-Align by Clustal W,选择所有序列,出现下图,所有参数为默认,点击OK。
5. 我们看到在未对齐之前,由于序列长度不一样,有些序列长出来很多,而有的序列在这些位点全是gap,为了排除gap位点的干扰。
我们需要将序列两端对齐。
两端以比对上最短的序列为准,删除其他序列5’和3’多余的部分,可以看到在序列比对上的部分,最上面一行软件标记为“*”,我们需要将没有标记“*”的位点删除,可以用shift一起选择没有标记“*”开始和末端的位点,选好后点击鼠标右键,单击delete删除。

利用MEGA 来构建进化树(molecular evolutionary genetics analysis 分子进化遗传分析)打开mega5,选择Align----edit/built alignment----create a new alignment—OK选择DNA/protein出现新的对话框Open------选择已经保存好的用clustalx 经过比对保存的以.aln格式的文件打开之后,出现下面的页面双击文件名可以进行修改的。
我的就是从这里开始修改把A,B,C 都去掉,只留号码就好右键菜单点击delete 删除带※的那一行。
得到下面的图示,点击保存,重新起名字。
之后点击此图内的Alignment 选择Align by clustalW即可。
默认设置即可,点击OK就进行比对了,此后会出现一个过渡对话框,显示的是两两比对和多序列比对的过程之后回到初始页面,就是这个页面之后点File---点开,把刚才保留的文件点开然后出现下面的页面多了几个内容,点击TA的那个框框。
之后出现这样的框框图片然后在主程序中选择phylogeny---construct/test neighbor-joining tree,然后出现下面的页面黄色框框处的的参数是可以改变的,该图为我已经改变好的,把Bootstrap 的值改为1000 Methods根据文献上的参考改为了Kimura2-parameter model.之后点击compute,就出现了,而且还带有必需的支持率即自展值,是用来检验你所计算的进化树分支可信度的。
简单地讲就是把序列的位点都重排,重排后的序列再用相同的办法构树,如果原来树的分枝在重排后构的树中也出现了,就给这个分枝打上一分,如果没出现就给0分,这样经过你给定的repetitions 次(至少1000次)重排构树打分后,每个分枝就都得出分值,计算机会给你换算成bootstrap值。
重排的序列有很多组合,值越小说明分枝的可信度越低,最好根据数据的情况选用不同的构树方法和模型。

如何用MEGA5.0和Clustalx1.83构建进化树MEGA是一个关于序列分析以及比较统计的工具包,从3.1版本到后来的4.0版本一直都广为大家熟悉,现在推出了Mega5.0版本。
功能比以前多有改进。
现主要介绍使用Mega 5.0构建系统进化树的方法。
供大家参考。
用MEGA构建进化树有以下步骤:1、测序:将克隆扩增测序得到的16S rDNA序列进行测序。
2、NCBI上做Blast/blast/Blast.cgi找到相似度最高的几个序列,确定一下你分离的细菌大约属于哪个科哪个属,如果相似度达到百分之百那基本可以确定你分离得到的就是Blast到的那个,然后寻找相似性最高的细菌,通常把该属的序列(Fasta格式文件)下载下来,或点击GenBank登录号,复制FSA TA 格式,整合在一个*.txt文档中(单独建立一个文件夹存放,后面的很多文件会自动装入该文件夹),如>XXXXAGGCTTAACACA TGCAAGTCGAGCGGAGCGAGGGTGCTTGCACCTTAGCTTAGCGGCG GACGGGTGAGTAA TGCTTAGGAA TCTGCCTA TTAGTGGGGGACAACA TTCCGAAAGGA A TGCTAA TACCGCA TACGCCCTACGGGGGAAAGCAGGGGA TCTTCGGACCTTGCGCTAA TAGA TGAGCCTAAGTCGGA TTAGCTAGTTGGTGGG>gi|289469964|gb|GU388381.1| Acinetobacter tandoii strain DSM 14970 16S ribosomal RNA gene, partial sequenceACTTAGCGGCGGACGGGTGAGTAA TGCTTAGGAA TCTGCCTA TTAGTGGGGGACAACA TTCCGAAAGGGA TGCTAA TACCGCA TACGCCCTACGGGGGAAAGCAGGGGA TCTTCGG ACCTTGCGCTAA TAGA TGAGCCTAAGTCGGA TTAGCTAGTTGGTGGGGTAAAGGCCTAC CAAGGCGACGA TCTGTAGCGGGTCTGAGAGGA TGA………………………….参考序列选择注意事项:1、不选非培养(unclutured)微生物为参比;2、不选未定分类地位的微生物,最相近的仅作参考;c,在保证同属的前提下,优先选择16S rDNA全长测序或全基因组测序的种;d,每个种属选择一个参考序列,如果自己的序列中同一属的较多,可适当选择两个参考序列。


使用mega构建进化树的流程下载温馨提示:该文档是我店铺精心编制而成,希望大家下载以后,能够帮助大家解决实际的问题。
文档下载后可定制随意修改,请根据实际需要进行相应的调整和使用,谢谢!并且,本店铺为大家提供各种各样类型的实用资料,如教育随笔、日记赏析、句子摘抄、古诗大全、经典美文、话题作文、工作总结、词语解析、文案摘录、其他资料等等,如想了解不同资料格式和写法,敬请关注!Download tips: This document is carefully compiled by theeditor. I hope that after you download them,they can help yousolve practical problems. The document can be customized andmodified after downloading,please adjust and use it according toactual needs, thank you!In addition, our shop provides you with various types ofpractical materials,such as educational essays, diaryappreciation,sentence excerpts,ancient poems,classic articles,topic composition,work summary,word parsing,copy excerpts,other materials and so on,want to know different data formats andwriting methods,please pay attention!使用 MEGA 构建进化树的流程如下:1. 数据准备:收集需要构建进化树的序列数据,可以是 DNA 序列或蛋白质序列。
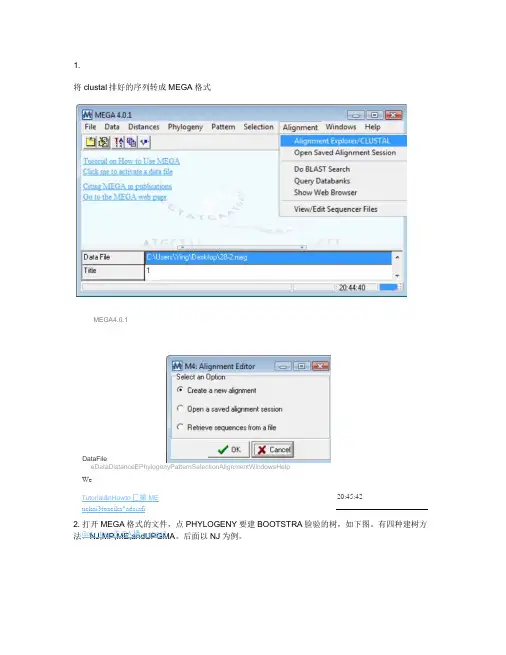
将clustal 排好的序列转成MEGA 格式
MEGA4.0.1
eDataDistanceEPhylogenyPatternSelectionAlignmentWindowsHelp
We 20:45:42
2.打开MEGA 格式的文件,点PHYLOGENY 要建BOOTSTRA 脸验的树,如下图。
有四种建树方法,NJ,MP,ME,andUPGMA。
后面以NJ 为例。
DataFile
Got 。
the 、正GA 橇,ebpa3 Tutorial&nHowto 匚第ME tickni3toacika*adaiafi
3。
点击NJ后如下图。
点击绿色方格可以改变BOOTSTRA呻重复的次数(>100), GAP是pairwise还是completedeletion(一般选PAIRWISE),适合你数据的替换
模型(有MODELTEST可以检验)。
(一定要根据自己的数据来设这些值)
4。
一切就绪后,点击COMPUTE结果如下,红圈中的数字就是bootstrap值,一般大于70%的枝认为比较有意义.
5。
如果有外类群,你可以直接点击你的外类群,得到有根树
网M4:Tre&Explcrer(C:\Use
FileImageSubtreeVie
口昌电配e t
AOriginaltreeIBootstrapc
RootonBranch
6。
基本过程就是这样,MEGA还有其他一些功能,希望大家继续补充。
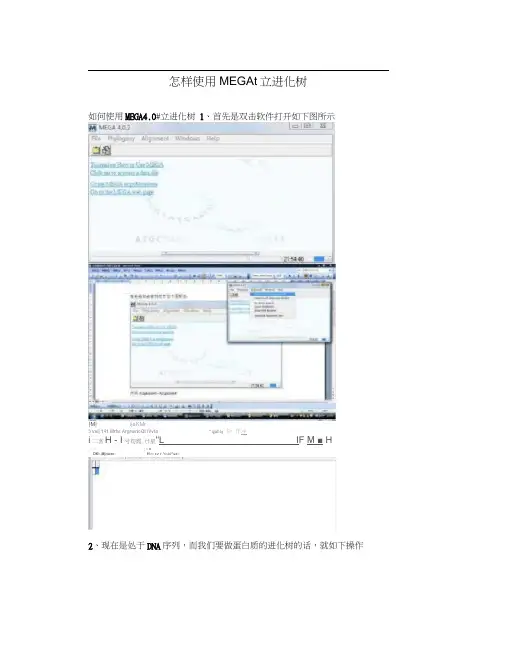
怎样使用MEGAt 立进化树如何使用MEGA4.0#立进化树 1、首先是双击软件打开如下图所示|M| ijaKMr3 valj 141 Mrhr ArgrwricQt iVvta“qplii :护 忏冲 i 二客H - I 号筍需.廿星"LIF M ■ H 、-| II ■ DKi -Mjrsrze: H r« r-r r ^c>az^ LCS2、现在是处于DNA序列,而我们要做蛋白质的进化树的话,就如下操作M4. Aligmr>&nl Explof頁H L lQnmt*Ftji Editm e祁3、接下来我们要进行序列的输入,点击左边那个红箭头,贝U出现下面的窗口刚M4: Alfgnment Explorer匚;日屯EJrt S«ar di Aflgmnenl Wfrb $e<)□ d| D ◎日「蹇輻酋1 41象Protein S^quer匚弊1|主曲色"匕色丄4、然后右击sequenee 1,修改名字,如改成DPVFrotejn Sequence?5、然后从Word里复制蛋白质序列,然后在下面的位置粘贴G 辱CopfPTCtfiT X CU,書 f sterna6则可出现如下图的序列了□ QCW1C3 iRWfl Wq^ri[ V^i>n irequ^Ki 幷册枷・1話皿讥曲佰i"—喇・ct Mgeirc 惟■ sy7、然后点击窗口上的保存图标保存 8、重复从3开始,直到你的序列输入完9、序列输入元后进行最后的保存,方法如下垂邑trit 5|讨之斗和"1 of op«r * dow亠 P TOUMT 1 <io-jrr<n接下来打开册b M 罗哥 H*lpi t X t tt b要输入ul7两次保存名字一然后关闭这个窗口出现下面这个窗口■■■MM Jfc接下来就可以建立各种样式的进化树〜乜 MdngHie-r jein^ IMJL* &? Wrigym 佔抽杓也山-« UW3ML ■> ■小h,鼻 陆01申*貝Trfl 和 Hi^Tgrn^ ,HnNkk T ivn HnM "d i-Oi^4*cflArs R 协 FriWrt '^l^diCNHE軒I 匚 fkrti tiiitanr-ri : hy A 护产就 匸沁”-嗯,只是把过程写出来,方便大家建立进化树,不足的地方,大家补充好〜。

MEGA6使用教程——进化树的构建首先,打开MEGA6软件。
在主界面上方的菜单栏中,选择“File”→“Open Data Directory”来选择数据目录。
在数据目录中,应该存在一个以.meg为文件格式后缀的文件,用于存储算法运行结果。
如果不存在这样的文件,可以通过“File”→“New”来创建一个新的.meg文件。
在.meg文件中,可以导入多种类型的数据,如DNA序列、蛋白质序列、线粒体DNA序列等。
点击菜单栏中的“Data”→“Import Alignment from File”来导入序列文件。
导入序列文件后,可以从菜单栏中的“Phylogeny”→“Construct/Test Maximum-Likelihood Tree”来构建最大似然进化树。
在弹出的对话框中,可以选择不同的进化模型来评估树的质量。
MEGA6提供了多种模型,如Jukes-Cantor模型、Kimura 2-parameter模型、Tamura 3-parameter模型等。
可以在下拉菜单中选择不同的模型。
计算完成后,可以在弹出的窗口上看到生成的进化树。
可以通过缩放、拖动、旋转等操作来查看树的不同部分。
此外,还可以使用MEGA6中的其他工具来分析和优化进化树。
比如,“Phylogeny”→“Switch Trees/Branches”工具可以帮助我们比较和切换不同的进化树。
此外,还可以使用“Phylogeny”→“Bootstrapping”工具来计算进化树的支持率。
Bootstrapping是一种统计方法,通过对原始数据集进行重抽样来评估进化树的支持强度。
在使用MEGA6构建进化树时,还应该注意一些问题。
首先,选择合适的进化模型对结果的准确性至关重要。
根据输入数据的特点,选择适当的模型来评估进化树会得到更可靠的结果。
其次,应该进行足够的计算重复次数,以确保所得到的进化树是可靠的。
足够的重复次数可以提高进化树的准确度和稳定性。
怎样使用MEGA建立进化树在进行生物信息学研究中,建立进化树是一项非常重要的任务。
MEGA (分子进化遗传学分析)是一款常用的软件,专门用于进行进化树和多序列分析。
下面将详细介绍如何使用MEGA建立进化树。
安装完成后,打开MEGA软件。
在MEGA的主界面上,有几个常用的功能选项,包括「File」、「Edit」、「View」、「Tools」、「Align」、「Phylogeny」和「Help」。
我们主要关注「Phylogeny」(进化树)选项。
在新窗口中,我们需要选择构建进化树的方法。
MEGA支持多种构建进化树的方法,包括Neighbor Joining、Maximum Parsimony、Maximum Likelihood和Bayesian等。
在这里,我们以Neighbor Joining方法为例进行演示。
在Neighbor Joining方法中,我们需要先选择计算进化距离的方法。
MEGA支持许多计算进化距离的方法,如P-distance、Kimura 2-parameter、Tamura 3-parameter等。
在这里,我们选择P-distance方法。
在选择了计算进化距离的方法后,我们还需要选择树的标准。
MEGA支持Bootstrap(Bootstrap方法是统计学中一种用于评估统计性信号和树的可靠性的方法)和Nearest-Neighbor Interchange等标准。
在这里,我们选择Bootstrap标准。
在选择了进化距离的方法和树的标准后,我们需要选择输入序列数据的文件格式。
MEGA支持多种格式的序列文件,如FASTA、PHYLIP和MEGA 等。
选择相应的格式后,我们需要导入序列数据。
可以通过从文件中导入或从剪贴板中粘贴来导入序列数据。
MEGA是一款非常强大的进化树分析软件,但对于初学者来说,可能需要一些时间去了解其中的各种选项和功能。
因此,建议在使用MEGA之前,先阅读相关文档和教程,以便更好地使用MEGA进行进化树的构建和分析。
进化树分析软件MEGA的用法MEGA(Molecular Evolutionary Genetics Analysis)是一款功能强大的分子进化遗传学分析软件,用于构建进化树、进行序列比对、计算基因组变异等。
它提供了丰富的功能和易于使用的界面,使用户能够对生物序列进行详细的进化分析。
下面是MEGA软件的用法详解。
1.安装和启动MEGA软件2.导入序列数据在MEGA软件中,可以导入多种类型的序列数据,如DNA序列、蛋白质序列等。
您可以通过"File"菜单下的"Open"选项来导入已有的序列文件,或通过粘贴操作将文本格式的序列数据直接粘贴到MEGA软件中。
3.序列比对MEGA提供了多种序列比对方法,如ClustalW、MUSCLE等。
您可以通过"Align"菜单下的"Multiple Sequence Alignment"选项选择适当的方法进行序列比对。
在比对完成后,软件将显示每个位置的序列相似性信息。
4.进化树构建MEGA支持多种进化树构建方法,如NJ法(Neighbor-Joining)、ML法(Maximum Likelihood)等。
您可以通过"Phylogeny"菜单下的"Construct/Inference Phylogenetic Trees"选项选择适当的方法进行进化树构建。
MEGA还支持Bootstrap分析,用于评估构建的进化树的可靠性。
6.进化分析MEGA提供了多个工具用于进一步研究和分析进化树上的数据。
通过"Phylogeny"菜单下的"Tree Explorer"选项,您可以对进化树进行多种分析,如比较进化树的拓扑结构、计算进化树的分支长度、分析基因组变异等。
7.分支针对性分析MEGA还提供了一些工具用于对进化树上的特定分支进行分析。
MEGA构建系统进化树的步骤(以MEGA7为例)本文是看中国慕课山东大学生物信息学课程总结出来的分子进化的研究对象是核酸和蛋白质序列。
研究某个基因的进化,是用它的DNA序列,还是翻译后的蛋白质序列呢?序列的选取要遵循以下原则:1)如果DNA序列的两两间的一致度≥70%,选用DNA 序列。
因为,如果DNA序列都如此相似,它的蛋白质会相似到看不出区别,这对构建系统发生树是不利的。
所以这种情况下应该选用DNA序列,而不选蛋白质序列。
2)如果DNA序列的两两间的一致度≤70%,DNA序列和蛋白质序列都可以选用。
1. 将要用于构建系统进化树的所有序列合并到同一个fasta格式文件,注意:所有序列的方向都要保持一致( 5’-3’)。
想要做系统发生树先要做多序列比对,然后把多序列比对的结果提交给建树软件进行建树,所以在用MEGA建树时可以输入一个已经比对好的多序列比对,也可以输入一条原始序列,让MEGA先来做多序列比对,再建树(一般我们都是原始序列)。
所以我们以后者为例。
2.打开MEGA软件,选择主窗口的”File”→“Open A File”→找到并打开fasta文件,这时会询问以何种方式打开,我们是原始序列,需要先进行多序列比对,所以选择“Align”。
如果是比对好的多序列比对可以直接选择“Analyze”。
3.在打开的Alignment Explorer窗口中选择”Alignment”-“Align by ClustalW”进行多序列比对(MEGA提供了ClustalW 和Muscle两种多序列比对方法,这里选择熟悉的ClustalW),弹出窗口询问“Nothing selected for alignment,Select all?”选择“OK”。
4. 之后,弹出多序列比对参数设置窗口。
这个窗口和EMBL在线多序列比对一样,可以设置替换记分矩阵、不同的空位罚分(罚分填写的是正数,计算时按负数计算)等参数。
进化树的建立过程
1,通过测序后,在NCBI中进行BLAST比对,看和哪个属中的种最近,从而确定进化树中需比较的菌种,然后可以在权威的International Journal of Systematic and Evolutionary Microbiology杂志中看最近是否有你要建树的菌的图,从而更捷径的得到典型的建树对比菌株(一般上标为T)
2,打开MEGA 4在Alignmen t→Query Databanks→
在空格处添加建树对比菌的登入号,然后直接点击上头的Add to Alignmen t
3 添加完对比的后,将自己测序菌株序列导入
如果拿回来后的序列是文本文档,就需要将它转化成fasta格式,其实也就是在文本文档上头加个“>”号就可以,但是序列字母必须是大写的,如果是小写的,可以在DNAman 中转化成大写的(或者在EditSeq中的先全选择序列后在edit的reverse case中转变,后如下操作),并且需每列中的数字去掉,保存为fasta格式后,
在MEGA的Edit→insert sequences to file将保存的fasta文件导入MEMA中,如果导入
的序列是互补链的话,直接在添加的里面,点击导入链,右击后点击互补就行,选中所有的序列后,在Alignmen t选项中选中Align by clustalw让其自动分析后,在Date选项中输出格式选择为MEGA格式保存
4 再一次启动软件将上一步保存的文件打开,然后在
如上图操作就可以得出进化树,然后在上面直接修改。
用MEGA 4构建进化树的过程
自己直接从NCBI对测序结果直接Blast,获得的比对结果选取同源性大于96%的序列,直接Download另存为.fasta格式,然后直接用MEGA打开一个序列,对下载的每个序列用记事本打开,检查序列的格式是否统一,再通过该软件的菜单栏的Edit→Insert Sequence From File(添加所要比对的的序列)→Alignment →Align by ClustalW→出现的界面点击OK→Data→Expert Alignment→MEGA Format(保存该文件并命名)→出现界面Protein Coding Nucleotide Sequence Data →点击NO→关闭该比对界面→出现界面Open The Data File in MEGA→点击YES→出现一个新界面,不用管它,点击另一个界面菜单Phylogeny→Bootstrap Test of Phylogeny→根据需要选择自己所要的进化树结构类型。
怎么样用MEGA建坐进化树之阳早格格创做是一个关于序列分解以及比较统计的工具包,其中包罗有距离建立法战MP建立法;可自动大概脚动举止序列比对付,估计进化树,估算分子进化率,举前进化假设考验,还能联机的Web数据库检索.下载后可间接使用,主要包罗几个圆里的功能硬件:i)DNA战蛋黑量序列数据的分解硬件.ii)序列数据转形成距离数据后,对付距离数据分解的硬件. iii)对付基果频次战连绝的元素分解的硬件.iv)把序列的每个碱基/氨基酸独力瞅待(碱基/氨基酸惟有0战1的状态)时,对付序列举止分解的硬件.v)画造战建矫正化树的硬件,举止网上blast搜索.用MEGA建坐进化树有以下步调:1. 16S rDNA测序战参照序列采用从环境中分散到单克隆,去沉复后扩删16S rDNA序列并测序,而后与数据库比对付,找到相似度最下的几个序列,决定一下您分散的细菌约莫属于哪个科哪个属,如果相似度达到百分之百那基础不妨决定您分散得到的便是Blast到的那个,而后找一到二个共科的,再找一到二个共脚段,再找一到二个共目的细菌,把序列齐脚下下去,以FSATA形式调整正在TXT文档中,如>TS1GCAGTCGAACGATGAAGCCCAGCTTGCTGGGTGGATT AGTGGCGAACGGGTGAGTAACACGTGGGTGATCTGCC CTGCACTTCGGGATAAGCCTGGGAAACTGGGTCTAAT ACCGGATAGGACCTCGGGATGCATGTTCCGGGGTGGA AAGGTTTTCCGGTGCAGGATGGGCC>gi|117572706|gb|EF028124.1| Rhodococcus sp. Atl25 16S ribosomal RNA gene, partial sequence CGATTAGAGTTTGATCCTGGCTCAGGACGAACGCTGGC GGCGTGCTTAACACATGCAAGTCGAACGATGAAGCCC AGCTTGCTGGGTGGATTAGTGGCGAACGGGTGAGTAA CACGTGGGTGATCTGCCCTGCACTTCGGGATAAGCCTG GGAAACTGGGTCTAATACCGGAT>TS2 TGCAAGTCGAGCGAATGGATTAAGAGCTTGCTCTTATG AAGTTAGCGGCGGACGGGTGAGTAACACGTGGGTAAC CTGCCCATAAGACTGGGATAACTCCGGGAAACCGGGG CTAATACCGGATAACATTTTGAACTGCATGGTTCGAAA TTGAAAGGCGGCTTCGGCTGTCACT GATGAACGCTGGCGGCGTGCCTAATACATGCAAGTCG AGCGAATGGATTAAGAGCTTGCTCTTATGAAGTTAGCG GCGGACGGGTGAGTAACACGTGGGTAACCTGCCCATA AGACTGGGATAACTCCGGGAAACCGGGGCTAATACCGGATAACATTTTGAA CYGCATGGTTC………………………….………………………….参照序列采用有几个准则:a,不选非培植(unclutured)微死物为参比;b,所选参照序列要精确,内里无过失碱基;c,正在包管共属的前提下,劣先采用16S rDNA齐少测序大概齐基果组测序的种;d,每个种属采用一个参照序列,如果自己的序列中共一属的较多,可适合采用二个参照序列. 2. 序列比对付将整治佳的序列导进,如图接着步调自动运止,得出截止,自动输出 .aln战.dnd 为后缀的二个文献.序列比对付也不妨间接用MEGA去搞.MEGA,如下图所示:4.只可挨启meg要领的文献,然而是它不妨把其余要领的多序列比对付文献变换过去,用.aln要领(Clustal的输出文献)变换.meg文献.面File:Convert to MEGA Format,挨启变换文献对付话框,从脚段文献夹中选中Clustal 对付比分解后所爆收的.aln文献,面打挨启.5. 变换佳的meg文献,会弹出一个提示疑息,面打ok.查看meg序列文献末尾是可平常,若存留clustal. *止,即可简略.面存盘保存meg文献,meg文献会战aln文献保存正在共一个目录.6. 关关变换窗心,回到主窗心,当前面里板上的“Click me to activate a data file”挨启刚刚才的meg文献.如果为蛋黑量序列,采用“protein sequence”,电打“OK”,得到以下图示,数据输进之后的格式,窗心底下有序列文献名战典型.而正在其余一个窗心内,出现以下数据文献面打采用战编写数据分类图标,可对付所采用的序列举止编写,完成后面打close即可.序列编写完成后,可举止保存,面打保存后出现以下界里,面打ok即可.7. 建坐进化树的算法主要分为二类:独力元素法(discrete character methods)战距离依赖法(distance methods).所谓独力元素法是指进化树的拓扑形状是由序列上的每个碱基/氨基酸的状态决断的(比圆:一个序列上大概包罗很多的酶切位面,而每个酶切位面的存留与可是由几个碱基的状态决断的,也便是道一个序列碱基的状态决断着它的酶切位面状态,当多个序列举前进化树分解时,进化树的拓扑形状也便由那些碱基的状态决断了).而距离依赖法是指进化树的拓扑形状由二二序列的进化距离决断的.进化树枝条的少度代表着进化距离.独力元素法包罗最大简约性法(Maximum Parsimony methods)战最大大概性法(Maximum Likelihood methods);距离依赖法包罗除权配对付法(UPGMAM)战邻位贯串法(Neighbor-joining).(1)phylogeny→UPGMA(2)用Bootstrap建坐进化树,MEGA的主要功能便是搞Bootstrap考证的进化树分解,Bootstrap考证是对付进化树举止统计考证的一种要领,不妨动做进化树稳当性的一个度量.百般算法虽然分歧,然而是支配要领基础普遍.进化树的建坐是一个统计教问题.咱们所建坐出去的进化树不过对付真正在的进化关系的评估大概者模拟.如果咱们采与了一个适合的要领,那么所建坐的进化树便会靠近真正在的“进化树”.模拟的进化树需要一种数教要领去对付其举止评估.分歧的算法有分歧的适用目标.普遍去道,最大简约性法适用于切合以下条件的多序列:i 所要比较的序列的碱基不共小,ii 对付于序列上的每一个碱基有近似相等的变同率,iii 不过多的颠换/变换的倾背,iv 所考验的序列的碱基数目较多(大于几千个碱基);用最大大概性法分解序列则不需以上的诸多条件,然而是此种要领估计极其耗时.如果分解的序列较多,有大概要花上几天的时间才搞估计完成.历程如下①参数的树坐:phylogeny→bootstrap test of phylogeny→NJ②系统进化树的尝试要领,不妨采用用Bootstrap,也不妨采用不举止尝试.沉复次数(Replications)常常设定起码要大于100比较佳,随机数种子不妨自己随意设定,不会做用估计截止.普遍采用500大概1000.有许多Model供采用,默认为Kimura 2-paramete r,分歧的Model 有分歧的算法,简曲请参照博业的死物疑息教书籍籍.设定完成,面compute,启初估计.②截止输出:那个历程所耗时间战序列的数量战少短成正比,步调便会爆收那样一个树,该窗心中有二个属性页,一个是本初树,一个是bootstrap考证过的普遍树.树枝上的数字表示bootstrap考证中该树枝可疑度的百分比.截止如下:8. 进化树的劣化:1)利用该硬件可得到分歧树型,如下图所示:除此除中,还不妨有多种树型,根据需要去采用.2)隐现建立的相关疑息:面打图标i.3)面打劣化图标,可举止各项劣化:Tree栏中,不妨举止树型采用:rectangular tree/circle tree/radiation tree.每种树皆不妨举止少度,宽度大概角度等的设定Branch:可对付树枝上的疑息举止建改.Lable:可对付树枝的名字举止建改.Scale:标尺树坐Cutoff:cutoff for consensus tree.普遍为50%. 9、进化树的分类劣化Place root on branch:不妨去回变换.Flip subtree:180度翻转分枝,名字翻转180度.Swab subtree:接换分枝,名字不翻转.Compress/expand subtree与Set divergent time:不妨把共一分枝的基果压缩大概扩展.面打Compress/expand subtree后,正在要压缩的分枝处面打,出现以下界里,正在name/caption 中输进文献名(比圆wwww),其余另有很多的选项,树坐佳了,面打OK.所得到的截止,不妨正在压缩战扩展之间变换. 10. 安排进化树根据所的进化树的效验,要举止安排,包罗多余序列简略、缺累序列增加、种属称呼标注等等,还要根据投稿纯志央供正在PHOTOSHOP中建改等.完成后的进化树应包罗充脚的疑息.自己所搞进化树完成图如下:。
如何使用MEGA4。
0建立进化树1、首先是双击软件打开如下图所示
2、现在是处于DNA序列,而我们要做蛋白质的进化树的话,就如下操作
3、接下来我们要进行序列的输入,点击左边那个红箭头,则出现下面的窗口;
4、然后右击sequence 1,修改名字,如改成DPV
5、然后从Word 里复制蛋白质序列,然后在下面的位置粘贴
6、则可出现如下图的序列了
7、然后点击窗口上的保存图标保存
8、重复从3开始,直到你的序列输入完
9、序列输入完后进行最后的保存,方法如下:
要输入ul7两次保存名字—然后关闭这个窗口. 接下来打开
出现下面这个窗口!
接下来就可以建立各种样式的进化树!
嗯,只是把过程写出来,方便大家建立进化树,不足的地方,大家补充好!。